Artículos
Variabilidad morfo-agronómica en genotipos de arroz en el Pacífico Central, Costa Rica
Morpho-agronomic variability in rice genotypes in the Central Pacific, Costa Rica
Variabilidad morfo-agronómica en genotipos de arroz en el Pacífico Central, Costa Rica
Ciencia y Agricultura, vol. 19, núm. 1, pp. 1-14, 2022
Universidad Pedagógica y Tecnológica de Colombia (UPTC)
Recepción: 03 Agosto 2021
Aprobación: 09 Febrero 2022
Resumen: El arroz (Oryza sativa L.) está incluido en la dieta alimenticia diaria del 75% de la población mundial. En Costa Rica, el sector arrocero es un eje fundamental de atención, particularmente porque es el principal producto dentro de la canasta básica alimentaria. Estudiar la variabilidad morfo-agronómica de este cereal es un factor clave para planificar estrategias de mejoramiento genético. El objetivo de la presente investigación fue determinar cuáles son los caracteres morfo-agronómicos que tiene un mayor aporte a la variabilidad genética en 54 líneas de arroz. Las líneas evaluadas provienen de una colección del banco de germoplasma del CIAT de Colombia, estas fueron enviadas a Costa Rica a través de la Corporación Nacional Arrocera (CONARROZ). Se midieron siete variables morfológicas cuantitativas y cinco cualitativas. Para las cuantitativas, se calculó el coeficiente de variación y se realizó un Análisis de Componentes Principales (PCA), así como un Análisis de Agrupamiento. Con las cualitativas se realizó un Análisis de Correspondencia Múltiple (MCA). Las variables cuantitativas más heterogéneas según los valores del coeficiente de variación fueron: toneladas por hectárea, tallos fértiles, y granos llenos por panícula. El PCA demostró que todas las variables, excepto la altura de la planta, aportaron a la varianza total, y el MCA sugiere que las variables cualitativas medidas en esta investigación, son discriminatorias para diferenciar genotipos. No se observó correlación entre las variables cuantitativas estudiadas. En el análisis de agrupamiento se obtuvo cuatro grupos de los cuales, uno de ellos abarcó la mayoría de los genotipos. Los genotipos de este último grupo se caracterizan por poseer altos valores para la variable granos llenos por panícula y valores medios y altos para el resto de las variables. Los resultados obtenidos son útiles para elegir las variables adecuadas para la selección. El análisis de conglomerados permitió establecer la relación filogenética entre las líneas para la planificación de futuros cruzamientos.
Palabras clave: PCA, MCA, Oryza sativa, caracteres morfológicos.
Abstract: Rice (Oryza sativa L.) is included in the daily diet of 75% of the world population. In Costa Rica, the rice sector is a fundamental axis of attention, particularly because it is the main product within the basic food basket. Studying the morpho-agronomic variability of this cereal is a key factor for planning breeding strategies. The objective of the present investigation was to determine which morpho-agronomic traits give the greater contribution to genetics in 54 rice lines. The evaluated lines come from a collection of the germplasm bank of CIAT in Colombia, these were sent to Costa Rica through the National Rice Corporation (CONARROZ). Seven quantitative and five qualitative morphological variables were measured. For the quantitative ones, the coefficient of variation was calculated and a Principal Component Analysis (PCA) was performed, as well as a Cluster Analysis. With the qualitative ones, a Multiple Correspondence Analysis (MCA) was performed. The most heterogeneous quantitative variables according to the values of the coefficient of variation were: tons per hectare, fertile stems and full grains per panicle. The PCA revealed that all the variables, except plant height, contributed to the total variance, and the MCA suggests that the qualitative variables measured in this research are discriminatory to differentiate genotypes. No correlations were reached between the quantitative variables studied. In the cluster analysis, four groups were obtained, one of which comprised the majority of the genotypes. The genotypes of this last group are characterized by having high values for the variable full grains per panicle and medium and high values for the rest of the variables. The results obtained are useful to choose the appropriate variables for selection. The cluster analysis allowed to establish the phylogenetic relationship between the lines for the planning of future crosses.
Keywords: PCA, MCA, Oryza sativa, morphological characters.
INTRODUCCIÓN
El arroz (Oryza sativa L.) es uno de los cereales de mayor producción a nivel mundial junto al trigo y al maíz y está incluido en la dieta alimenticia diaria del 75% de la población mundial (GRiSp, 2013). El grano de arroz está constituido por un 75% a 80% de almidón, 12% de agua y 7% de proteína, y es un alimento básico en muchos lugares del mundo, incluidos algunos países en desarrollo (Oko et al., 2012; Hossain et al., 2009).
En Costa Rica, las tendencias globalizantes y de libre comercio, convierten al sector arrocero en un eje fundamental de atención, porque es el principal producto de la canasta básica alimentaria, con un consumo promedio per cápita de 51,78 kg para el 2000-2013 (Sánchez y Vega, 2018).
La tasa de crecimiento de la población mundial exige un aumento en el rendimiento de este cereal. El desarrollo de cultivares de alto rendimiento requiere la implementación de un programa de mejoramiento genético, para lo cual es importante conocer la variabilidad genética dentro del germoplasma (Oladosu et al., 2014; Nidhi et al., 2019). La estrecha variabilidad genética existente en las variedades de arroz modernas provoca que sean más vulnerables a estrés biótico y abiótico, lo cual explica la tasa más lenta de progreso genético alcanzada últimamente por los mejoradores (Baderinwa-Adejumo, 2012; Kumbhar et al., 2015).
El conocimiento de la diversidad genética entre cultivares en una región es importante para planificar estrategias de mejoramiento y reducir la vulnerabilidad genética, debido a apariciones repentinas de plagas o enfermedades (Berrio-Orozco et al., 2016). La diversidad genética puede ser evaluada a través de marcadores morfológicos, fisiológicos y bioquímicos (Zúñiga-Orozco y Carrodeguas-González, 2020).
En Costa Rica, se reportan estudios sobre variabilidad genética de variedades de arroz pertenecientes al CIAT en años anteriores. Berrio-Orozco et al (2016), estudiaron la variabilidad genética mediante el análisis del pedigrí de 51 cultivares de arroz por tanto no realizaron observaciones de tipo morfológico, molecular o de isoenzimas. El análisis de agrupamiento les permitió separar a los genotipos en catorce grupos distintos, donde existen materiales relacionados. No obstante, los autores recomendaron realizar estudios posteriores basados en marcadores genéticos debido a que, los análisis de pedigrí se basan en el supuesto de que cada progenitor aporta el 50% de los genes, por lo que constituyen una aproximación de la diversidad genética existente.
En otras latitudes se realizaron evaluaciones de genotipos de arroz obtenidos por hibridación, a través de caracteres morfo-agronómicos. Fue posible determinar las variables más importantes para la caracterización, las cuales fueron: rendimiento, masa de 1000 granos, panículas por metro cuadrado, granos llenos y vanos por panículas (Díaz et al., 2015).
Teniendo como punto de partida los antecedentes enunciados, esta investigación tiene como objetivo determinar cuáles son los caracteres morfológicos que aportan variabilidad genética en 54 líneas de arroz de interés para los programas de mejora genética en Costa Rica.
MATERIALES Y MÉTODOS
Ubicación
El ensayo se realizó durante el 2019 en la Finca La Bandera (9° 52’ latitud norte y 84°32’ longitud oeste), propiedad de CONARROZ, que se ubica en el cantón de Parrita, provincia de Puntarenas, con una temperatura promedio de 27°C, humedad relativa de 80% y precipitación promedio anual de 2500 mm.
Material vegetal
De la totalidad del banco de germoplasma de arroz que maneja el CIAT en Colombia fueron solicitadas específicamente 54 líneas por parte de la Corporación Nacional Arrocera (CONARROZ). Estas líneas se estudiaron para incluirlas en el programa de mejoramiento de CONARROZ y constituyó un único ensayo para estos fines. Se utilizaron como testigos 4 líneas comerciales de Costa Rica: Palmar 18, Conarroz 1, Nayuribe y Lazarroz.
Diseño experimental
El experimento se llevó a cabo a través de un diseño de bloques aumentados de Federer, puesto que, el diseño permite la comparación de gran cantidad de materiales (Aguade, 2013; Rojas-Martínez, 2005). El material vegetal se distribuyó en 3 bloques, cada uno estuvo compuesto por dos bloques con 18 líneas, uno con 15 líneas y en cada bloque se incluyó 4 testigos comerciales, los cuales fueron colocados al azar. Cada parcela de cada línea estuvo constituido por 7 surcos de 5 m lineales con distancia entre ellos de 15 cm. La distancia entre bloques fue de 1,3 m. Las labores culturales (preparación del terreno, siembra, fertilización, riego y tratamientos fitosanitarios) se efectuaron según (Tinoco y Acuña, 2009) y el plan de manejo de la finca experimental de CONARROZ.
Variables morfológicas
Se evaluaron siete variables cuantitativas: (DF) días para 50% de floración (unidades), (AP) altura de la planta (cm), (LP) longitud de la panícula (cm), (TH) toneladas por hectárea (tn/ha), (TF) tallos fértiles (unidades), (P1000) peso de 1000 gramos (g) y (GLP) granos llenos por panícula (unidades). También se registraron cinco variables cualitativas (Tabla I). Todas las variables fueron seleccionadas tomando como referente la escala categórica propuesta por el Sistema Estandar de Evaluación para arroz propuesto por el International Rice Research Institute (IRRI) (SES, 2002).

Análisis de los datos
Para el procesamiento estadístico de las variables cuantitativas, se determinaron los parámetros de dispersión de la media (X), desviación estándar (ES) y coeficiente de variación (CV).
Se efectuó un Análisis de Componentes Principales (PCA) para las variables cuantitativas en el programa InfoStat(R) versión 2019, sobre la base de la matriz de correlaciones fenotípicas, con la finalidad de estudiar las variables más heterogéneas. Posteriormente se realizó un análisis de conglomerados utilizando la distancia Euclideana2.
Con las variables cualitativas se realizó un Análisis de Correspondencia Múltiple (MCA).
RESULTADOS Y DISCUSIÓN
Coeficiente de variación para variables cuantitativas
La tabla II muestra los caracteres con mayor variabilidad según el coeficiente de variación: toneladas por hectárea (CV=27.7%), tallos fértiles (CV=24.8%), y granos llenos por panícula (CV= 23.5%). Mediante el coeficiente de variación se observa la variabilidad en los caracteres morfológicos cuantitativos (Zúñiga-Orozco et al., 2020). Valores altos de CV corresponden a variables heterogéneas mientras que valores bajos a variables homogéneas. CV con valores altos indican que los atributos pueden ser utilizados en la identificación y selección de plantas con caracteres superiores (Garnica et al., 2020).
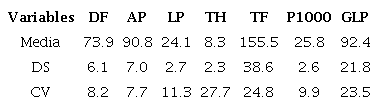
Díaz et al. (2004) evaluaron ocho variedades de arroz en Cuba, se obtuvo valores de CV muy bajos para las variables peso de 1000 gramos (0.83%), granos llenos por panícula (2.21%) y altura de la planta (0.89%). Igualmente, Díaz et al. (2013) evaluaron 8 variedades de arroz en Japón obteniendo bajos valores de CV para las variables: granos llenos por panícula (13.84%) y peso de 1000 gramos (2.51%). En el presente estudio coinciden con un CV bajo las variables, peso de 1000 granos y altura de planta, sin embargo, la variable granos llenos por panícula tiene mayor CV.
En el presente estudio, el alto valor de CV para la variable granos llenos por panícula se vio favorecido por la mayor cantidad de genotipos evaluados (54), en comparación con el estudio de Díaz et al (2004), en el cual, se evaluaron únicamente ocho genotipos. Un germoplasma de mayor tamaño es recomendable para aumentar la probabilidad de que exista variabilidad y que ésta sea amplia, sobre todo si se utilizan materiales de diverso origen.
Uzzaman et al. (2015) evaluaron 16 variedades de arroz en Bangladesh y obtuvieron valores de CV similares a los obtenidos en el presente estudio para las variables: altura de la planta (8.5%) y longitud de la panícula (10.9%), no siendo así para la variable días para la floración (1.1%). Konate et al. (2016) obtuvieron un CV similar en las variables días al 50% de floración y peso de 1000 granos, sin embargo, para las variables altura de planta y tallos fértiles.
Análisis de Componentes Principales
El análisis de componentes principales extrajo el 84% de la variabilidad original en los cuatro primeros componentes (Tabla III), lo que indica que los resultados de las correlaciones aproximadas obtenidas entre variables agronómicas pueden interpretarse confiablemente (González et al., 2010).

En un estudio realizado por Gour et al. (2016) donde se analizaron 83 genotipos de arroz en la India, se obtuvo 14 componentes explicando el 92,8% de la variabilidad total, sin embrago fueron consideradas las 5 primeras componentes para el análisis de datos. Sohgaura et al. (2015) encontraron 12 componentes principales con una variabilidad total del 93,9%.
Mientras más genotipos sean analizados más probabilidad existe de que la variabilidad sea mayor y, por tanto, sean necesarios más componentes para explicar la variación de los datos. En el presente estudio se analizó un menor genotipos de arroz y para explicar la variabilidad solo fue necesario tomar en cuenta cuatro componentes principales.
El PCA es un método estadístico que permite la fácil identificación de caracteres poligénicos que son de importancia en los programas de mejora genética. En dichos programas es relevante determinar cuáles variables contribuyen más a la variabilidad genética del germoplasma para ser tomadas en cuenta durante la selección. Los valores de las variables en cada componente son positivos o negativos. Independientemente del signo, estos valores pueden ser utilizados para estimar la contribución de cada variable a la variabilidad de cada componente principal (Singh et al., 2020).
En la Tabla IV se puede observar el aporte de cada variable a las cuatro primeras componentes. En el primer componente, la variable de mayor contribución fue longitud de la panícula (0.58), en el segundo, toneladas por hectárea (0.52) y tallos fértiles por panícula (0.52), en el tercero, peso de 1000 gramos (-0.55) y en el cuarto componente, días a floración (0.66) y peso de 1000 gramos (-0.54).
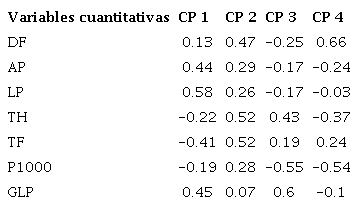
La única variable que no mostró una contribución significativa fue altura de la planta, siendo en el análisis anterior la de menor CV (Tabla II). Sin embargo, en la figura 1 se puede observar que, aunque el valor de vector propio no fue alto, comparado con otras variables, si hay contribución en el primer componente. Por tanto, no es la variable más discriminatoria para el germoplasma evaluado. En otros estudios similares, se demostró su contribución a la varianza total. Por ejemplo, Díaz et al. (2013) obtuvieron contribución significativa en el PCA para las variables, granos llenos por panículas, altura de la planta y peso de 1000 gramos.

Figura 1
Material vegetal evaluado durante el experimento a los 110 días después de la siembra. Parrita, Puntarenas, Costa Rica.
Fuente: autor
Es importante determinar las variables que más contribuyen a la varianza puesto que indican cuales deben seleccionarse. Nidhi et al. (2019) reportaron en arroz, que las variables más importantes son: días a floración, días a la madurez, ton/ha y peso de 1000 granos como las variables más importantes.
En la figura 2 se puede apreciar fácilmente la contribución de cada variable a la varianza total, situándose a la izquierda las de contribución negativa.
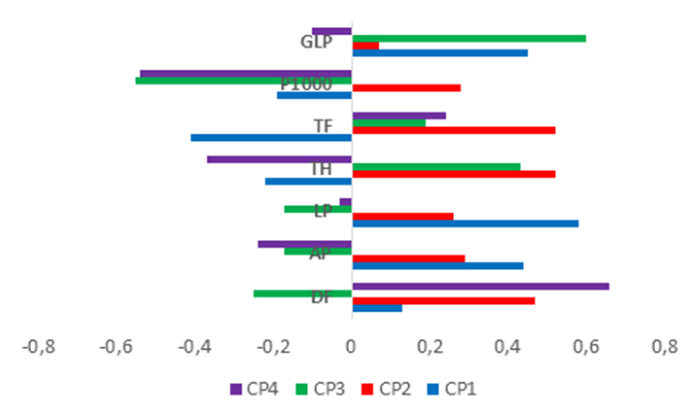
Figura 2
Contribución de cada variable a la varianza de los 4 componentes en el PCA.
Los valores obtenidos en el CPA pueden utilizarse para proponer índices de selección precisos, cuya intensidad puede decidirse por la variabilidad explicada por cada uno de los componentes principales. Una puntuación alta para un germoplasma, en un componente en particular indica valores altos para las variables (Gour et al., 2016).
Correlación entre variables cuantitativas
La matriz de correlaciones obtenida en el PCA entre cada par de variables analizadas, se presenta en la Tabla V. Se observa que no hay altas correlaciones en las variables estudiadas. Díaz et al., (2017) y Zhang et al. (2015) reportaron la no existencia de correlación entre la variable altura de la planta con el resto de las variables tomadas, lo cual coincide con los resultados del presente estudio para dicha variable.
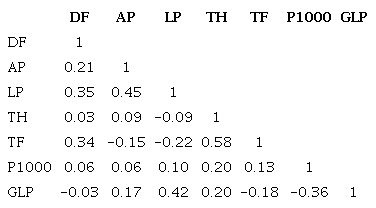
Por otra parte, Díaz et al., (2017) y Rashid et al. (2014) reportaron correlaciones fuertes y directas entre las variables peso de 1000 granos y granos llenos por panículas, mientras en el presente estudio no se detectó dicha relación. Konate et al. (2016) reportaron correlaciones bajas para diferentes variables excepto para la relación t ha-1 y biomasa.
Análisis de agrupamiento según variables cuantitativas
Tomando en cuenta los resultados del PCA, el cual sugiere que todas las variables contribuyen a la varianza excepto la altura de la planta, se realizó un análisis de agrupamiento utilizando la distancia Euclideana 2. En la figura 3 se observa el cladograma obtenido.
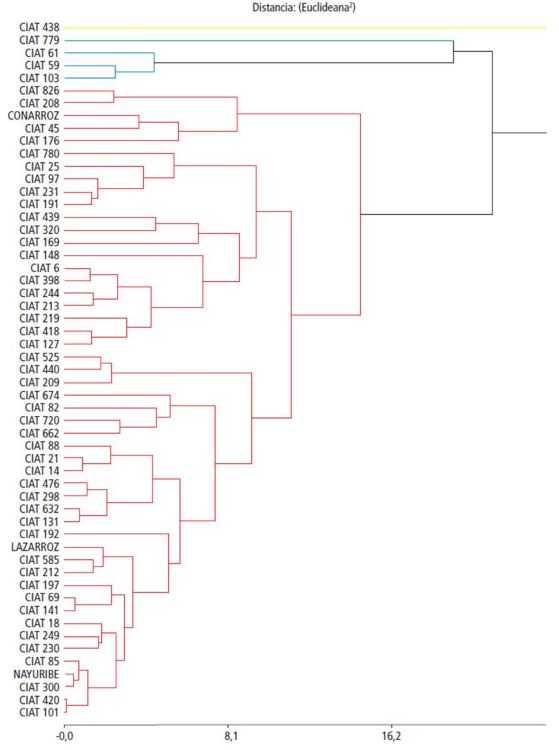
Figura 3
Cladograma obtenido según el análisis de conglomerados.
Se puede observar en la figura 3, que, tomando como punto de corte, la distancia de ligamiento en 16.2, se forman 4 grupos de genotipos de arroz.
El primer grupo (color rojo) está conformado por la mayoría de los genotipos que se caracterizan por altos valores para la variable granos llenos por panícula y valores medios y altos para las variables peso de 1000 granos, tallos fértiles, toneladas por hectárea, longitud de la panícula y días a floración (CONARROZ, LAZARROZ, NAYURIBE, Palmar 18, CIAT 6, CIAT 14, CIAT 127, CIAT 585, CIAT 131, CIAT 320, CIAT 439, CIAT 244, CIAT 19CIAT 191, CIAT 780, CIAT 197, CIAT 25, CIAT 298, CIAT 82, CIAT 213, CIAT 169, CIAT 101, CIAT 45, CIAT 720, CIAT 398, CIAT 148, CIAT 88, CIAT 632, CIAT 249, CIAT 97, CIAT 476, CIAT 21, CIAT 826, CIAT 231, CIAT 420, CIAT 85, CIAT 662, CIAT 219, CIAT 440, CIAT 230, CIAT 300, CIAT 525, CIAT 209, CIAT 674, CIAT 141, CIAT 59, CIAT 208, CIAT 418, CIAT 212, CIAT 69 y CIAT 176.
El segundo grupo (color azul) está conformado por los genotipos CIAT 61 y CIAT 59, los cuales se caracterizan por presentar valores muy bajos de las variables granos llenos por panícula.
El tercer grupo (color amarillo) está conformado por el genotipo CIAT 438, el cual se diferencia del resto por presentar valores muy altos de tallos fértiles y además demora más días para la floración.
El cuarto grupo (color verde) está conformado por el genotipo CIAT 779, el cual presentó valores muy bajos de la variable granos llenos por panícula.
Análisis de Correspondencia múltiple para variables cualitativas
Para el Análisis de Correspondencia Múltiple se identificaron 3 dimensiones que explican el 89% de la variabilidad total. La primera dimensión explica el 40% de la variación total y estuvo asociada con las variables vigor a los 15 días y a los 45 días. La segunda dimensión explica el 33% de variación total a través de las variables acame y aceptación fenotípica. La tercera dimensión explica el 16% de la variación original y la variable que contribuyó a la inercia de esta fue la exerción de la panícula (Fig. 4).
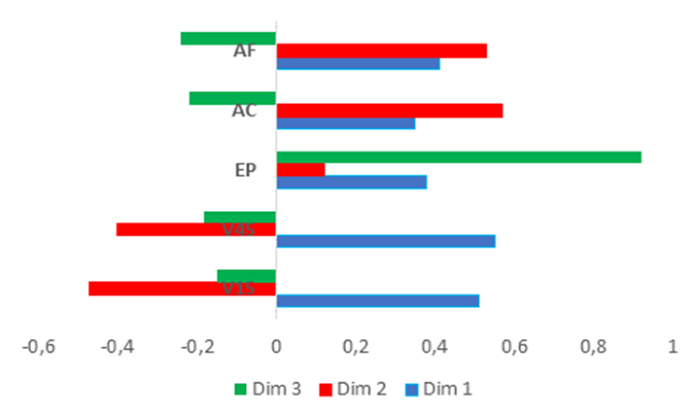
Figura 4
Contribución de cada variable cualitativa analizada a la inercia de cada una de las 3 dimensiones formadas en el MCA.
El MCA permite estudiar las relaciones de interdependencia entre variables categóricas, es decir, no métricas y de esta forma guarda cierta analogía con la prueba X2 (Ji-cuadrado) (Aranzazu et al., 2007). Este método estadístico se utiliza para reducir la dimensionalidad de los datos y analizar la relación existente entre las variables, por tanto, permite saber que variables cualitativas contribuyen a la varianza total (Gámez, 2012).
De este análisis se puede concluir, que las variables cualitativas tomadas en cuenta en el presente estudio también son discriminatorias y por tanto pueden ser tomadas en cuenta para analizar la variación del germoplasma y caracterizarlo.
CONCLUSIONES
Según los valores del CV las variables más heterogéneas fueron: toneladas por hectárea, tallos fértiles y granos llenos por panícula, por tanto, la mejora de estos caracteres es posible dentro de este germoplasma.
El PCA demostró que todas las variables, excepto la altura de la planta aportaron a la varianza total, por lo que pueden ser tomadas en cuenta en programas de mejoramiento.
No se observó una correlación alta en ninguna de las variables, lo que implica que para este germoplasma los caracteres no están relacionados.
En el análisis de agrupamiento se obtuvo cuatro grupos, de los cuales uno de ellos abarcaba la mayoría de los genotipos analizados y esto se debe a que se presentaron valores altos para la variable “granos llenos por panícula” y valores medios y altos para el resto de las variables.
El análisis de correspondencia múltiple sugiere que las variables cualitativas medidas en esta investigación, son discriminatorias y pueden ser utilizadas para estudiar variación en el germoplasma, así como establecer relaciones filogenéticas entre las líneas.
REFERENCIAS
Aguade A. (2013). Construction and analysis of augmented and modified augmented designs. Saarbrücken, Germany: Lambert Academic Publishing.
Aranzazu D.A., Rodríguez B.J., Zapata M.M., Bustamante J. y Restrepo L.F. (2007). Application of Multiple correspondence factor analysis to a heart valve study in pigs.Rev. Col. Cienc. Pec.,20: 129-140.
Baderinwa-Adejumo A.O. (2012). Potentials of agrobotanical characters of some local rice germplasm (Oryza sativaL.) for improved production in nigeria.Journal of Science and Science Education, 3(1): 111-117.
Berrio-Orozco L.E., Torres-Toro E.A., Barona-Valencia J. y Cuásquer-Sedano J. B. (2016). Diversidad genética de las variedades de arroz FLAR liberadas entre 2003-2014. Agron. Mesoam., 27(2): 217-231.
Díaz S.H., Cristo E., Morejón R., Castro R., Shiraishi M., Dhanappala M.P. y Keisuke A. (2013). Análisis de la estructura productiva y comportamiento de rendimiento de cuatro variedades de arroz (Oryza sativa L.) de diferentes orígenes en la prefectura de Ibaraki, Japón. Cultivos Tropicales. 34(1): 42-50.
Díaz S.H., Morejón R. y Pérez N.J. (2017). Behavior and selection of rice advanced lines (Oryza sativa L.) obtained by Breeding Program in Los Palacios. Cultivos Tropicales, 38(1): 81-88.
Díaz S.H., Morejón R., Castro R., Pérez N. y González M. (2004). Evaluación de variedades de arroz (Oryza sativa L.) para la época de primavera en Pinar del Río. Cultivos Tropicales, 25(4): 77-81.
Díaz S.H., Morejón R.; Onicka O. y Castro R. (2015). Evaluación de nuevas líneas de arroz (Oryza sativa L.) obtenidas por hibridaciones dentro del Programa de Mejoramiento Genético del cultivo en Cuba. Cultivos Tropicales, 36(3): 115-123.
Gámez N. (2012). Fundamentos y aplicaciones del análisis de correspondencias difuso. Comunicaciones en Estadística, 5(1): 7-32.
Garnica J.P., Rodríguez O.J., Jaramillo-Barrios C.I. y Vallejo F.A. (2020). Morphological Diversity and Selection Characters of Arracacha (Arracacha xanthorriza Bancr.) Germoplasm in Colombia. Ciencia y Agricultura, 17(3): 49-62. DOI: https://doi.org/10.19053/01228420.v17.n3.2020.11150
González A.D., Pérez J., Sahagún J., Franco O., Morales E.J., Rubí M., Gutiérrez M.F. y Balbuena A. (2010). Aplicación y comparación de métodos univariados para evaluar la estabilidad en maíces del Valle Toluca-Atlacomulco. México. Rev. Agronomía Costarr, 34, 129-143.
Gour L., Maurya S.B, Koutu G.K, Singh S.K., Shukla S.S. y Mishra D.K. (2016). Characterization of rice (Oryza sativa L.) genotypes using principal component analysis including scree plot & rotated component matrix. International Journal of Chemical Studies, 5(4): 975-983.
GRiSP (Global Rice Science Partnership), 2013. Rice Almanac, 4th edition. International Rice Research Institute. Los Baños, Filipinas: IRRI Library.
Hossain M.S., Singh A.K. y Fasihuz-Zaman. (2009). Cooking and eating characteristics of some newly identified inter sub-specific (indica/japonica) rice hybrids. Science Asia, 35: 320-25. DOI: https://doi.org/10.2306/scienceasia1513-1874.2009.35.320
Konate A., Zongo A., Kam H., Sanni A. y Audebert S. (2016). Genetic variability and correlation analysis of rice (Oryza sativa L.) inbred lines based on agromorphological traits. Afric. Jrnl. Agric. Res., 11(35): 3340-3346. DOI: https://doi.org/10.5897/AJAR2016.11415
Kumbhar S.D., Kulwal P.L., Patil J.V., Sarawate C.D., Gaikwad A.P. y Jadhav A. S. (2015). Genetic Diversity and Population Structure in Landraces and Improved Rice Varieties from India. Rice Science, 22(3): 99-107. DOI: http://dx.doi.org/10.1016/j.rsci.2015.05.013
Nidhi D., Raj S., Prasad M., Khatri N. y Raj B. (2019). Genetic Variability and Correlation Coefficients of Major Traits in Early Maturing Rice under Rainfed Lowland Environments of Nepal. Advances in Agriculture, 5975901. DOI: https://doi.org/10.1155/2019/5975901
Oko A., Ubi B., Efisue A., Efisue, A. y Nahemiah, D. (2012). Comparative analysis of the chemical nutrient composition of selected local and newly introduced rice varieties grown in Ebonyi state of Nigeria. Intern. Jrnl. Agric. Forestry, 2(2):16-23.
Rashid K., Kahliq I., Farooq M.O. y Ahsan M.Z. (2014) Correlation and Cluster Analysis of some Yield and Yield Related Traits in Rice (Oryza Sativa). Journal of Recent Advances in Agriculture, 2(8): 290-295.
Rojas-Martínez B. (2005). Bloques aumentados (Repaso: Federer, 1961). Agrociencia, 39(6): 693-695.
Sánchez Y. y Vega M.F. (2018). Situación del mercado del arroz en Costa Rica: una mirada a la realidad. Revista ABRA, 38(56): 1-22. DOI: https://doi.org/10.15359/abra.38-56.1
SES, (2002). Standar evaluation system for rice. International Rice Research Institute (IRRI). Los Baños, Filipinas: IRRI Library .
Singh P., Jain P.K. y Tiwari A. (2020). Principal Component Analysis Approach for Yield Attributing Traits in Chilli (Capsicum annum L.) Genotypes. Chemical Science Review and Letters, 9(33): 87-91.
Sohgaura N., Mishra D.K., Koutu G.K., Singh K., Kumar V. y Singh P. (2015). Evaluation of high yielding and better quality rice varieties using principal component analysis. Eco. Env. & Cons., (21):187-195.
Tinoco R. y Acuña A. (2009). Manual de recomendaciones técnicas en el cultivo de arroz. Instituto Nacional de Innovación y Transferencia en Tecnología Agropecuaria (INTA). http://www.mag.go.cr/biblioteca_virtual/bibliotecavirtual/a00177.pdf
Uzzaman T., Sikder R.K., Asif M.I., Mehraj H. y Jamal-Uddin A.F.M. (2015). Growth and Yield Trial of Sixteen Rice Varieties under System of rice Intensification. Scientia Agriculturae, 11(2): 81-89. DOI: https://doi.org/10.15192/PSCP.SA.2015.11.2.8189
Zhang B., Ye W., Ren D., Tian P., Peng Y., Gao Y., Ruan B., Wang L., Zhang G., Guo L., Qian Q. y Gao Z. (2015). Genetic analysis of flag leaf size and candidate genes determination of a major QTL for flag leaf width in rice. Rice, 8(2). DOI: http://dx.doi.org/10.1186/s12284-014-0039-9
Zúñiga-Orozco A. y Carrodeguas-González A. (2021). Echeveria (Crassulaceae): Potencial para la mejora genética como ornamental. Avances en Investigación Agropecuaria. 25(3): 57-81.
Zúñiga-Orozco A., Carrodeguas-González A. y Chinchilla-Obando M. (2021). Variabilidad morfoagronómica de poblaciones F2 de pimiento (Capsicum annuum L.) en Cartago, Costa Rica. Avances en Investigación Agropecuaria. 25(2): 53-67.
Notas
