Artículo científico
Microbioma Rizosférico de Bacterias en Maíz Criollo de Grano: Impacto Sobre el Rendimiento Bajo Transición Agroecológica
Rhizospheric Microbiome of Bacteria in Creole Grain Maize: Impact on Yield Under Agroecological Transition
Microbioma Rizosférico de Bacterias en Maíz Criollo de Grano: Impacto Sobre el Rendimiento Bajo Transición Agroecológica
Terra Latinoamericana, vol. 41, e1664, 2023
Sociedad Mexicana de la Ciencia del Suelo A.C.
Recepción: 15 Abril 2023
Aprobación: 28 Junio 2023
Resumen: El maíz es un cereal de importancia en términos de nutrición humana y animal a nivel mundial. En el presente estudio se comparó el microbioma bacteriano de la rizosfera del suelo entre tres razas criollas de maíz ( Zea mays L .), forrajero (C1), doble propósito (C2) y grano (C3); asimismo se determinó su impacto sobre el rendimiento. Se trabajó en parcelas ubicadas en el Campo Experimental El Retiro de la Universidad Autónoma Agraria Antonio Narro (UAAAN). El muestreo de suelo se efectuó el 13 de junio del 2021, 51 días después de la siembra. El DNA se extrajo a partir de tres muestras de cada tipo de raza de maíz. Se amplificó la región V3-V4 del gen 16S rRNA y se realizó secuenciación masiva de siguiente generación con Illumina; el análisis bioinformático se desarrolló en QIIME utilizando la referencia taxonómica bacteriana EzBioCloud. El phylum Proteobacteria, la clase Phycisphaerae, los órdenes Shingomonadales, Micrococcales y Phycisphaerales, las familias Moroxellaceae, Micrococcaceae, Chitinophagaceae, Shingobacteriaceae y Enterobacteriaceae, así como los géneros Acinetobacter, Shingobacterium y Cryseobacterium, fueron los taxa bacterianos que difirieron en abundancia relativa entre las tres razas ( P < 0.05, prueba Kruskal-Wallis y una disimilitud promedio > 0.10 en el análisis SIMPER). Dentro de los taxa mencionados se detectaron bacterias promotoras de crecimiento vegetal (BPCV) como Acinetobacter y Sphingobacterium. Se concluye que, de las razas analizadas, la C2 mostró los mejores rendimientos de peso del grano (15.56 Mg ha -1) y peso seco en forraje (10.61 Mg ha -1), la cual representa una buena opción para preservar la semilla y realizar investigaciones posteriores bajo diferentes condiciones.
Palabras clave: Acinetobacter, Moroxellaceae, Proteobacteria, secuenciación, Sphingobacterium.
Summary:
Maize is an important cereal in terms of human and animal nutrition worldwide. In our study, the bacterial microbiome composition of the soil rhizosphere was compared among three maize (
Zea mays L.) races: forage (C1), dual-purpose (C2) and
grain (C3). Additionally, the impact of the bacterial microbiome of the soil rhizosphere over yield was determined. Our study was conducted in plots located in the El Retiro Experimental Field at Universidad Autónoma Agraria Antonio Narro (UAAAN). Soil sampling was carried out in June 13, 2021, 51 days after sowing. DNA was extracted from three samples of each maize race. The V3-V4 region of the 16S rRNA gene was amplified and massive next-generation sequencing was performed with Illumina. The bioinformatic analysis was conducted in QIIME using the bacterial taxonomic reference of EzBioCloud. The phylum Proteobacteria, the class Phycisphaerae, the orders Shingomonadales, Micrococcales and Phycisphaerales, the families Moroxellaceae, Micrococcaceae, Chitinophagaceae, Shingobacteriaceae and Enterobacteriaceae, as well as the genera
Acinetobacter,
Shingobacterium and
Cryseobacterium, were the bacterial taxa that differed in relative abundance among the three races (
P < 0.05, Kruskal-Wallis test and an average dissimilarity > 0.10 in the SIMPER analysis). Among the taxa identified, plant growth promoting bacteria (PGPB) such as
Acinetobacter and
Sphingobacterium were detected. The race C2 showed the best yields of grain weight (15.56 Mg ha
-1) and forage dry weight (10.61 Mg ha
-1). Thus, we conclude that C2 represents a good option to preserve the seed and that further research should be developed for this race under different conditions.
Index words: Acinetobacter, Moroxellaceae, Proteobacteria, sequencing, Sphingobacterium.
Introducción
El maíz es el cereal más producido en todo el mundo según los últimos datos de la Organización para la Agricultura y la Alimentación, con una superficie cosechada de 205 ×10 6 ha y una producción de 1210 × 10 6 Mg en el año 2021, superando al arroz y al trigo en cuanto a productividad ( FAOSTAT, 2021), debido a que entre los cereales posee el más alto valor nutricional ( Singh, Singh y Singh, 2020), es considerado un componente importante para la alimentación humana y animal. En México el cultivo del maíz es el más representativo por su importancia cultural, económica y social ( SAGARPA, 2017). Dentro de la clasificación del maíz se encuentra el criollo que durante años ha sido mejorado por los campesinos, al realizar un intercambio de semillas mediante la selección empírica y con ello, intercambio de genes (Sánchez-Hernández, De la Cruz y Sánchez, 2015). Como resultado de esta selección existen diferentes razas de maíz, clasificadas según sus características isoenzimáticas y morfológicas ( Sánchez, Goodman y Stuber, 2000). Navarro-Garza, Hernández, Castillo y Pérez (2012) destacan que el término raza, en las plantas, se refiere al conjunto de características o fenotipo y que se le asigna un nombre el cual evidencia alguna asociación en especial. En México existe un reporte de 64 razas de maíz, de las cuales 59 se consideran nativas y cinco que fueron descritas inicialmente en otras regiones ( CONABIO, 2020).
En cuanto a rendimiento, el maíz criollo se ve superado considerablemente por las variedades mejoradas, no obstante, los pequeños agricultores se inclinan por las variedades nativas dado que poseen algunas ventajas, entre las cuales se encuentran: a) la capacidad para sembrarse en terrenos edáfica y climáticamente más limitados ( Turrent, Wise y Garvey, 2012), reportándose razas que sobreviven donde los maíces mejorados no lo hacen ( Vázquez-Carrillo, Pérez, Hernández, Marrufo y Martínez, 2010); b) aptitud para elaborar platillos tradicionales; c) estabilidad y adaptabilidad frente a climas locales y fluctuantes; d) reducción de costos en insumos para su producción; y e) mejor manejo del riesgo agrícola ( Guillén-Pérez, Sánchez, Mercado y Navarro, 2002; Turiján-Altamirano, Damián, Ramírez, Juárez y Estrella, 2012; Turrent et al., 2012 ). La Secretaría de Agricultura y Desarrollo Rural (SADER), informó que en 2020 la producción de maíz grano fue de 27 707 775 toneladas, mientras que en 2021 se reportó un crecimiento de 2.6% en la producción con una estimación de 28 427 436 toneladas ( SADER, 2021).
El factor edáfico comprende las propiedades físicas, químicas y biológicas, las cuales influyen en el desarrollo de las plantas ( Rajakaruna y Boyd, 2008). Dentro de las características biológicas del suelo, las comunidades microbianas son elementales en el desempeño de las plantas, al controlar su fisiología y crecimiento, siendo muy grande la diversidad microbiana, asociada con las raíces de las plantas ( Karnwal, 2022). La rizósfera se define como el suelo más próximo a las raíces de una planta, y el término “rizobacteria” engloba aquellas bacterias que están asociadas a dichas raíces en la rizósfera, las cuales pueden tener un efecto benéfico, neutral o dañino para la misma planta ( Odelade y Babalola, 2019). Entre las rizobacterias se encuentran las bacterias promotoras del crecimiento vegetal (BPCV), grupos de diversas especies que mejoran el crecimiento de las plantas ( González y Fuentes, 2017). Estas bacterias simbióticas que habitan la rizósfera de ciertas especies del maíz, además de favorecer su productividad, también participan en la defensa de la salud del cultivo sin dañar al ambiente ( Akhtar, Qureshi, Iqbal, Ahmad y Khan, 2012; Raza, Ling, Yang, Huang y Shen, 2016).
Cada vez hay más estudios que demuestran que el genoma de la planta tiene un impacto dinámico y directo en la estructura de su microbioma ( Aira, Gómez, Lazcano, Bååth y Domínguez, 2010; Cregger et al., 2018 ), este último definido como “… todo el hábitat, incluidos los microorganismos (bacterias, arqueas, eucariotas inferiores, superiores y virus), sus genomas (es decir, genes) y las condiciones ambientales circundantes…” ( Marchesi y Ravel, 2015). Considerando la asociación existente entre el genoma y el microbioma de la planta, es indispensable sopesar de manera conjunta al hospedero y el microbioma para fortalecer el conocimiento sobre el funcionamiento de la planta como un holobionte ( Ravanbakhsh, Kowalchuk y Jousset, 2020). Por lo tanto, el estudio del microbioma bacteriano rizosférico es fundamental para comprender el rendimiento de la planta. En el caso del maíz, el rendimiento tiene una relevancia considerable debido a que, a nivel regional y nacional, se espera un aumento continuo de la población, de ahí que la demanda de este cereal se incremente para ser destinado al consumo humano y animal. El presente estudio fue realizado sobre una transición agroecológica, cuestión imprescindible en la actualidad, ya que las técnicas agroecológicas aseguran un uso sostenible de los recursos naturales, el cuidado del ambiente y de las personas, permitiendo que se pueda garantizar la alimentación de cada familia a largo plazo. En atención a lo descrito anteriormente, el objetivo del presente estudio fue, describir el microbioma rizosférico de bacterias y su impacto sobre el rendimiento en tres razas de maíz criollo de grano, utilizadas en la producción de forraje, grano y doble propósito.
Materiales y Métodos
Ubicación y condiciones ambientales del área de estudio
La Comarca Lagunera presenta una precipitación pluvial promedio anual de 258 mm, con temperatura media anual de 21 °C, con máxima y mínima de 33.7 y 7.5 ºC, respectivamente ( Montemayor-Trejo et al., 2012 ). Se recolectaron muestras del microbioma rizosférico de suelo (franco-arenoso, pH 8.1, C.E. 1.8 mS cm -1, materia orgánica de 1.1%) del Campo Experimental El Retiro, de la Universidad Autónoma Agraria Antonio Narro, ubicado en el municipio de Francisco I. Madero, Coahuila de Zaragoza, México (25º 49’ 53.45” N y 103º 7’ 4.03” O), durante el desarrollo de tres razas de maíz criollo, para las cuales se ocuparon semillas del banco de germoplasma del Departamento de Agroecología de la propia institución: C1, raza forrajera; C2, raza doble propósito (grano y forraje) y C3, raza para grano, cada una con tres repeticiones etiquetadas como C1-1, C1-2, C1-3, C2-1, C2-2, C2-3, C3-1, C3-2 y C3-3.
Establecimiento del cultivo y manejo de las muestras
La siembra del cultivo, de las tres razas, de maíz criollo se efectuó el 13 de junio del 2021 en melgas de 120 m de largo y 10 m de ancho. Los surcos presentaron una separación de 0.75 m y una distancia entre plantas de 0.20 m. Las razas se sembraron en dos surcos de 60 m con cuatro repeticiones, y dos surcos de bordo entre éstas. La preparación del suelo consistió en doble rastreo, bordeo, con la aplicación de un riego de pre siembra de 0.20 m y se aplicaron cuatro riegos de auxilio de 0.15 m de lámina cada uno, utilizando un sistema de multi-compuertas. Se aplicó biol como repelente y fertilizante foliar cada ocho días, a los 40 días después de sembrado. El manejo de maleza se realizó de manera manual en una ocasión con dos jornales. A los 51 días se realizó el muestreo de la rizósfera. Se extrajo la planta de maíz y se obtuvieron 100 mg de suelo asociado a las raíces. Cada muestra fue colocada en un tubo bashing bead Zymo Research TM con 750 µL de buffer lisante/estabilizador Xpedition TM; estos tubos se procesaron en un disruptor celular TerraLyzer TM, durante 45 segundos, para la lisis celular y la conservación del DNA. Posteriormente, las muestras se transportaron al laboratorio en hielera portátil.
Extracción de DNA del microbioma del suelo
El DNA de las muestras se extrajo utilizando el kit DNA MiniPrep de Zymo Research TM y se cuantificó con un nanodrop ThermoScientific. Para efectuar la amplificación de la región V3-V4 del gen 16S rRNA se utilizaron los primeros propuestos por Klindworth et al. (2012) : S-D-Bact-0341-b785-a-A-21, 5´CCTACGGGNGGCWGCAG-3´ y S-D-Bact-0785-a-A-21, 5´-GACTACHVGGGTATCTAATCC-3´, con los cuales se generó un amplicón de ~460 pb. Se empleó el protocolo de PCR Illumina (2021a), suministrando 12.5 µL de MyTaq TM Ready Mix 1X (Bioline ®), 1 µL de cada primer (10 uM), 5 µL de DNA (50 ng totales) y 5.5 µL de H 2O grado molecular. Se utilizó el siguiente ciclo: 95 °C, por 3 minutos; 25 ciclos de 95 °C, durante 30 segundos, 55 °C por 30 segundos, 72 °C durante 30 segundos; 72 °C por 5 minutos, en un termociclador Labnet Multigene TM Gradient PCR. Se efectuó la purificación de los amplicones con perlas Agentcourt ® AMpure ® XP al 0.8%. Posteriormente, los amplicones se etiquetaron utilizando el Nextera XT Index Kit TM con ayuda del protocolo de Illumina (2021b), aplicando 25 µL de MyTaq TM Ready Mix 1X (Bioline ®) 5 µL de cada primer (N7xx y S5xx), 5 µL de DNA y 10 µL de H 2O, grado molecular; se empleó el siguiente ciclo: 95 °C por 3 minutos; 10 ciclos de 95 °C durante 30 segundos; 55 °C por 30 segundos, 72 °C durante 30 segundos; 72 °C por 5 minutos. Se efectuó la purificación de las bibliotecas con perlas Agentcourt ® AMpure ® XP al 1.2%. Para concluir, se llevó a cabo la cuantificación, normalización (equimolaridad) y secuenciación masiva de siguiente generación (MiSeq Illumina ® de 2 × 250 lecturas de final pareado) empleando el protocolo para metagenómica 16S ( Illumina, 2021a).
Análisis bioinformático
El análisis de las secuencias se efectuó en máquina virtual Oracle ® VM VirtualBox ® 6.1.34 en plataforma Linux, por medio del software bioinformático Quantitative Insights Into Microbial Ecology (QIIME) v.1.46 ( Caporaso et al., 2010 ). El proceso comenzó con el ensamblaje de las secuencias, forward y reverse, de las muestras, utilizando el programa PEAR ( Zhang, Kobert, Flouri y Stamatakis, 2014) con un traslape de 50 pb, una mínima longitud por lectura de 430 pb y máxima de 470 pb, con un criterio de calidad Q30 (una base errónea por cada 1000 bases) de acuerdo con lo recomendado por García-de la Peña et al. (2019) . Posteriormente, se transformaron los archivos a formato FASTA y se realizó la eliminación de secuencias quiméricas de las muestras con USEARCH ( Edgar, 2010).
Para la selección de las Unidades taxonómicas operacionales (OTUs) se aplicó el método UCLUST ( Edgar, 2010) al 97% de similitud; se seleccionó al azar una secuencia representativa para cada OTU y se realizó la asignación taxonómica, utilizando como referencia la base de datos EzBioCloud ( Yoon et al., 2017 ). Se elaboró el cuadro de OTUs en formato Biological observation matrix (Biom) ( McDonald et al., 2012 ), se realizó la separación de los dominios y se filtraron los singletons (OTUs que solo tuvieron una observación) de acuerdo con Navas-Molina et al. (2013) . Con los datos registrados se obtuvo la abundancia absoluta de OTUs y con esta información se graficó el número de secuencias por número de taxa para visualizar la profundidad de cobertura (curvas de tendencia asíntota); aplicando el programa PAST ver. 4.10 ( Hammer, Harper y Ryan, 2001).
Para los análisis ecológicos y estadísticos se realizó un proceso de rarefacción aleatoria simple ( Weiss et al., 2017 ) empleando como referencia el menor valor de las secuencias bacterianas, después de la eliminación de los singletons. Con el archivo estandarizado generado se calculó la diversidad alfa mediante los índices de Shannon y Simpson; para observar diferencia significativa en estos índices, entre las tres razas de maíz se emplearon pruebas no paramétricas de Kruskal-Wallis ( P < 0.05) y pruebas de comparación de medias de índices para cada raza. Para la diversidad beta se utilizó el índice de Bray-Curtis ( Beals, 1984), cuya matriz se empleó para efectuar una prueba PERMANOVA ( P < 0.05) buscando diferencia significativa entre las microbiotas de las tres razas de maíz criollo. La visualización de la diversidad beta se realizó mediante una gráfica de análisis de coordenadas principales (PCoA) utilizando el programa Emperor ( Vázquez-Baeza, Pirrung, Gonzalez y Knight, 2013). Las abundancias relativas para phylum, clase, orden, familia y género se analizaron en Microsoft Excel 2019. Los géneros con una abundancia ≥ 1% fueron representados en un mapa de calor; para la elaboración de dendrograma, de las muestras, se utilizó el método de conglomerados jerárquicos con medida euclidiana en el programa de libre acceso en línea Morpheus, Broad Institute. Finalmente, se llevó a cabo un análisis SIMPER y pruebas no paramétricas de Kruskal-Wallis a las rizobacterias encontradas entre las tres razas de maíz criollo, para cuantificar la contribución significativa de los taxa en las diferencias observadas con el índice de Bray-Curtis.
Se realizó la selección de las 100 mejores mazorcas, de las cuales se eligieron 10, basadas en el tamaño y peso, consideradas como las mejores en cada raza; para cada una se determinó su peso, utilizando una báscula digital marca Santul , además, se registraron datos de número de hileras, número de granos por hilera, peso del grano y olote. Con estos datos se determinó el rendimiento, contemplando la densidad de plantas (67 000 plantas ha -1).
Resultados y Discusión
La media del total de secuencias obtenidas antes del ensamblaje fue de 35 607; las secuencias ensambladas fueron 33 142 y se descartaron 2465 secuencias. Se eliminaron en promedio 3608 secuencias quiméricas y la media de secuencias de calidad fue 29 523. Después de la asignación taxonómica y de la eliminación de los singletons se obtuvo un promedio de 21 134 secuencias bacterianas y finalmente se registraron 6853 OTUs bacterianos sin singletons ( Cuadro 1). Las OTU en la raza C1 fueron 31 phyla, 88 clases, 171 órdenes, 380 familias, 977 géneros y 1059 especies; en la raza C2, 27 phyla, 86 clases, 164 órdenes, 364 familias, 973 géneros y 1040 especies; y la raza C3, 28 phyla, 84 clases, 163 órdenes, 351 familias, 937 géneros y 1012 especies. Se presentó una apropiada profundidad de cobertura referente al número de OTUs bacterianos de las muestras, dado que todas las curvas lograron la asíntota alrededor de las 13 000 secuencias ( Figura 1).
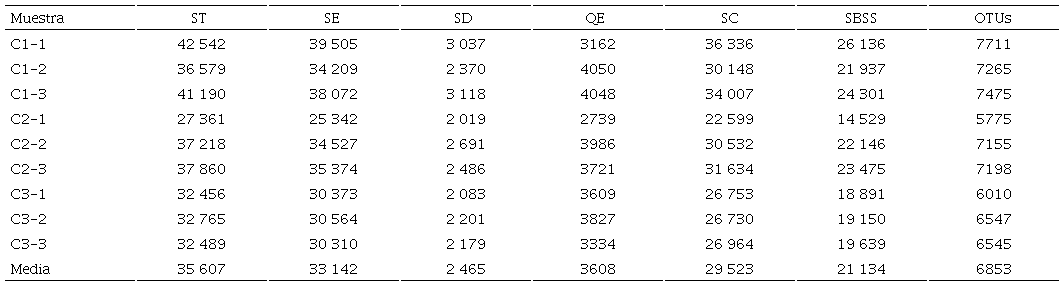
C1 = criollo 1; C2 = criollo 2; C3 = criollo 3; 1 a 3 = repeticiones; ST = secuencias totales; SE = secuencias ensambladas; SD = secuencias descartadas; QE = quimeras eliminadas; SC = secuencias de calidad después de la eliminación de quimeras; SBSS = Secuencias bacterianas después de la eliminación de los singletons; OTUs = unidades taxonómicas operacionales. C1 = creole 1; C2 = creole 2; C3 = creole 3; 1 to 3 = replicates; ST = total sequences; SE = assembled sequences; SD = discarded sequences; QE = chimeras removed; SC = quality sequences after chimeras removal; SBSS = bacterial sequences after singletons removal; OTUs = operational taxonomic Units.
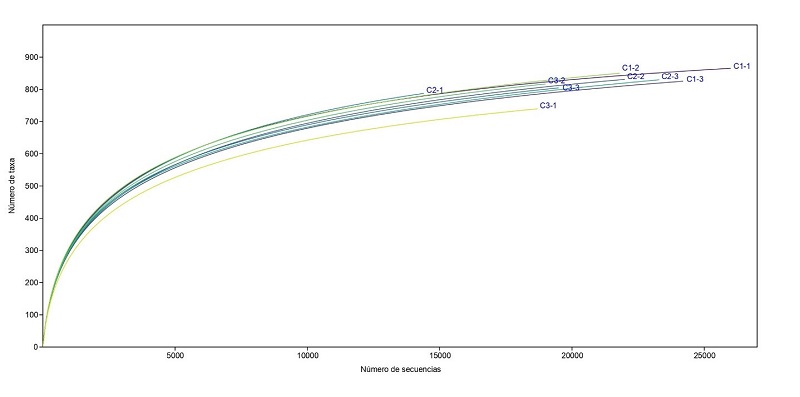
Figura 1:
Profundidad de cobertura de secuencias bacterianas rizosféricas de tres razas de maíz criollo (C1 = forraje, C2 = doble propósito y C3 = grano) con tres repeticiones.
En un estudio realizado por Peiffer et al. (2013a) demostraron que el genotipo Z. mays, spp., mays influye significativamente en la diversidad bacteriana alfa y beta. En cuanto a la diversidad alfa se observó que no existió diferencia significativa entre las tres razas de maíz criollo, con respecto a los índices de Shannon y Simpson (prueba de Kruskal-Wallis y medias de índices para cada raza de maíz). Es probable que la significancia en el índice de Simpson para la raza C3 se deba a los exudados de las raíces y al genotipo ( Peiffer y Ley, 2013b), lo cual coincide con lo que afirma Nazir et al. (2016) sobre los exudados de las raíces, que éstas están estrechamente relacionadas al reclutamiento de los microorganismos como son las BPCV. Se observó diferencia significativa en la diversidad beta entre las tres razas de maíz criollo (PERMANOVA: pseudo-F = 1.178, p = 0.007). En la gráfica de coordenadas principales ( Figura 2) se aprecia la agrupación compacta del grupo C2-1, C2-2 y C2-3; el grupo C1-1, C1-2 y C1-3 aparecen como un grupo más heterogéneo que el anterior, pero aun formando un grupo distinguible; por otra parte, las muestras C3-1, C3-2 y C3-3 registraron la mayor heterogeneidad individual y no formaron un grupo definido. En general, se aprecia que las tres razas de maíz criollo fueron distintas en cuanto a su diversidad bacteriana ( Figura 2).
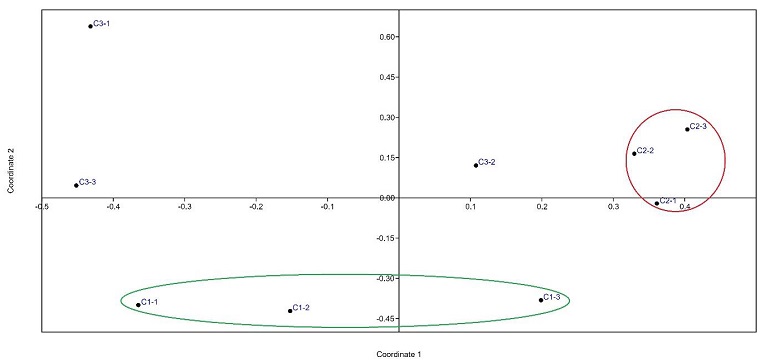
Figura 2:
Análisis de coordenadas principales basado en el índice de similitud de Bray-Curtis de la rizósfera bacteriana de las tres variedades de maíz criollo (C1 = forraje, C2 = doble propósito, C3= grano) con tres repeticiones.
Investigaciones previas que han utilizado herramientas moleculares para estudiar la composición de la comunidad bacteriana del suelo in situ demostraron que, aunque las bacterias se han subdividido en más de 100 phyla, menos de 10 son abundantes en el suelo ( Janssen, 2006). En el presente estudio se reportaron 31 phyla: los tres más abundantes para C1, C2 y C3, respectivamente, fueron Proteobacteria ( = 30, 33 y 35%), seguido de Actinobacteria ( = 19, 18 y 17%) y Acidobacteria ( = 13, 13 y 12%); mientras tanto, Gemmatimonadetes ( = 10, 11 y 10%), Chloroflexi ( = 9, 7 y 8%), Bacteroidetes ( = 5, 6 y 6%) y Planctomycetes ( = 5%) resultaron ser los menos frecuentes ( Figuras 3a, 3b). Una tendencia similar fue reportada por Qaisrani et al. (2019) , quienes concluyeron, a través de diversas investigaciones, que es claro que estos phyla suelen ser las bacterias más dominantes en la rizósfera del maíz. De la misma manera, Nemergut et al. (2011) destacan, además, que la abundancia relativa estimada de los principales phyla varía entre diferentes suelos o muestras.
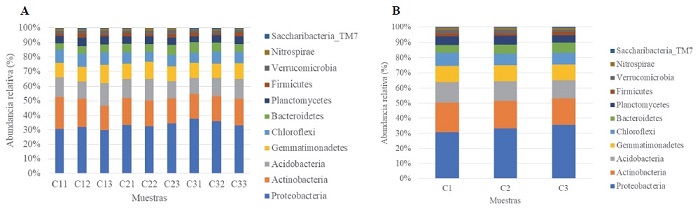
Figura 3:
a) Abundancia relativa (%) por muestra de maíz criollo y b) Abundancia relativa media (%) por raza de maíz criollo (promedio de tres repeticiones) de los phyla bacterianos rizosféricos más abundantes.
Para las tres razas de maíz C1, C2, C3, se registraron 96 clases taxonómicas de las cuales Alphaproteobacteria ( = 18, 19 y 20%), Actinobacteria_c ( = 11%), Vicinamibacter_c ( = 8.8 y 7%), Gammaproteobacteria ( = 5.6 y 7%), Gemmatimonadetes_c ( = 6.6 y 5%), Longimicrobia ( = 5%) y Deltaproteobacteria ( = 4%) fueron las más abundantes. A nivel de orden se obtuvieron 185 taxa de los cuales Sphingomonadales ( = 7.8 y 9%), Vicinamibacter_o ( = 8.8 y 7%), Gemmatimonadales ( = 6.6 y 5%), Rhizobiales ( = 5%), Rhodospirillales ( = 4.5 y 4%), Myxococcales ( = 3%) y Gaiellales ( = 3%) mostraron los porcentajes más altos. En cuanto a familias se reportaron 414 taxa donde predominaron Shingomonadaceae (= 6.7 y 8%), Vicinamibacter_f ( = 7.7 y 6%), Gemmatimonadaceae ( = 4.3 y 3%), Gaiellaceae ( = 3%), GQ263235_f ( = 3%), Rhodospirillaceae ( = 3%) y Tepidisphaeraceae ( = 3.2 y 3%). Asimismo, se obtuvieron 1164 géneros de los cuales los más abundantes fueron: Sphingomonas ( = 6.6 y 7 %), Gaiella ( = 3%), PAC001846_g ( = 3.3 y 2%), PAC001874_g ( = 3.2 y 2%), Tepidisphaera ( = 3.2 y 3%), PAC000624_g ( = 2%) y Steroidobacter ( = 2%).
De las 1283 especies registradas solo 14 de ellas poseen nombre taxonómico binomial: Allorhizobium borbori, Amycolatopsis keratiniphila, Bacillus subtilis, Enterobacter cloacae, Goodfellowiella coeruleoviolacea, Kallotenue papyrolyticum, Kibdelosporangium aridum, Klebsiella pneumonia, Neochlamydia hartmannellae, Nonomuraea roseoviolacea, Parachlamydia acanthamoebae , Photorhabdus luminescens, Roseomonas gilardii y Streptomyces thermoviolaceus; sin embargo, ninguna de ellas presentó una abundancia relativa mayor al 1%. En la Figura 4 se presenta un mapa de calor de las rizobacterias a nivel género con una abundancia relativa mayor al 1% de cada muestra edáfica de las tres razas de maíz criollo.
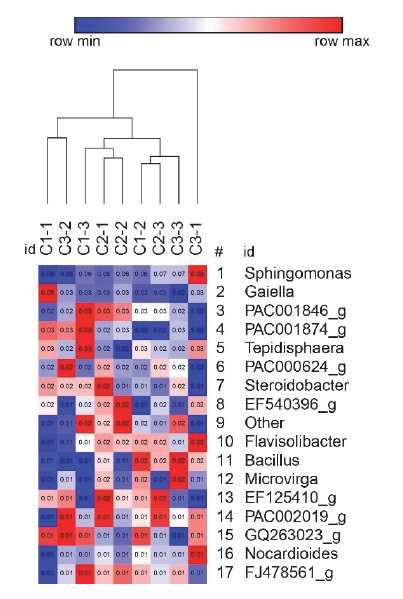
Figura 4:
Mapa de calor de las rizobacterias a nivel género (solo taxa bacterianos con abundancia relativa mayor al 0.01%) de cada muestra de suelo de las tres variedades de maíz criollo (C1 = forraje, C2 = doble propósito, C3= grano) con tres repeticiones.
Sphingomonas (Proteobacteria) fue el género más abundante en los tres maíces criollos estudiados ( Figura 4); este género posee diversas cualidades entre las cuales se encuentran: a) ser en un buen candidato para utilizarse como fertilizante biológico dado sus aptitudes para fijar N 2 ( Sun, Zhang, Xu y Hu, 2010); b) ser una BPCV que solubiliza potasio ( Etesami, Emami y Alikhani, 2017), y por ser una alfa-proteobacteria posee una sorprendente habilidad para degradar contaminantes ambientales recalcitrantes ( He et al., 2017 ) como pesticidas ( Manickam, Reddy, Saini y Shanker, 2008) o herbicidas ( Keum, Lee y Kim, 2008), considerándose como una excelente opción para la biorremediación ( Peng et al., 2008 ); y por último, c) algunas de sus cepas producen ciertos compuestos antibióticos que pueden ser responsables, de forma parcial, del control de algunas infecciones fúngicas que suelen infectar los maíces domesticados ( Chagas, Pessotti, Caraballo y Pupo, 2018).
Gaiella fue el segundo género más abundante en las tres razas de maíz. A pesar de que sus funciones son desconocidas, al pertenecer al phylum Actinobacteria posee diversas aptitudes que corresponden a una BPCV ( Yadav et al., 2018 ), favoreciendo la concentración de N, la materia orgánica y los micro y macroelementos esenciales en el suelo, así como el metabolismo del carbono y el desarrollo de las plantas ( AbdElgawad et al., 2020 ); adicionalmente, es un phylum que suele ser persistente en suelos áridos ( Santos-Medellin, Edwards, Liechty, Nguyen y Sundaresan, 2017) ya que puede sobrevivir en temperaturas mesófilas y algunos de sus miembros en temperaturas termófilas que alcanzan los 60 °C ( Edwards, 1993), protegiendo a los cultivos de los efectos negativos de la sequía ( Chukwuneme, Babalola, Kutu y Ojuederie, 2020).
Le prosiguen en abundancia los géneros no cultivables PAC001846_g y PAC001874_g, miembros de Acidobacteria, phylum que colabora con los miembros de Proteobacteria para degradar los polisacáridos fúngicos y vegetales ( Lladó, Žifčáková, Větrovský, Eichlerová y Baldrian, 2016; Zimmermann, Gonzalez y Saiz, 2006), describiéndose como el que tiende a incrementar su abundancia cuando el pH del suelo decrece ( Männistö, Tiirola y Häggblom, 2007; Jones et al., 2009 ; Dimitriu y Grayston, 2010).
Sphingomonas, Steroidobacter, Microvirga y EF125410_ g pertenecen a Proteobacteria, el phylum más abundante en el estudio, relevante para el ciclo global del nitrógeno, del azufre y del carbono con el fin de asegurar los procesos de los ciclos biogeoquímicos sostenibles ( Itävaara, Salavirta, Marjamaa y Ruskeeniemi, 2016); de la misma manera, tienen un papel fundamental en la degradación de la materia orgánica ( Coates, Cole, Chakraborty, O’Connor y Achenbach, 2002; Chaudhry, Rehman, Mishra, Chauhan y Nautiyal, 2012; Lladó et al., 2016 ) para producir una gran cantidad de alcoholes aromáticos y oligosacáridos que suelen ser utilizados como fuente de carbono por las acidobacterias ( Wei et al., 2017 ), aumentando la abundancia de estas últimas (PAC001846_g, PAC001874_g y PAC002019_g).
Tepidisphaera (Planctomycetes) es un phylum que se encuentra, comúnmente en las aguas termales terrestres y en diversos suelos de forma natural, inclusive encontrándose en diferentes sistemas productivos agrícolas e industriales ( Kovaleva et al., 2019 ); en el presente estudio respecto a las tres razas de maíz, obtuvo el quinto lugar en abundancia relativa. Los géneros PAC000624_g, EF540396_g y “other” pertenecen a Gemmatimonadetes, phylum que suele representar aproximadamente del 1-2% de las bacterias del suelo a nivel mundial ( Delgado-Baquerizo et al., 2018 ), siendo uno de los grupos menos estudiados; asimismo, al ser cosmopolitas en suelos, son capaz de acoplarse a un amplio abanico de nutrientes al tener un metabolismo versátil ( Mujakic, Piwosz y Koblizek, 2022), con la propiedad de adaptarse a ambientes secos, incrementando su abundancia en suelos áridos y semiáridos ( Acosta-Martínez, Dowd, Sun y Allen, 2008; Kim, Dungan y Crowley, 2008; Cary, McDonald, Barrett y Cowan, 2010; Neilson et al., 2017 ; Ahmed, Verma, Gupta, Mandhan y Chauhan, 2018; Zhao et al., 2020 ); esto tiene gran trascendencia debido a que la Comarca Lagunera se ubica dentro de la zona árida de México.
Por su parte, Flavisolibacter pertenece al phylum Bacteroidetes , este último caracterizado por estar involucrado en la degradación de moléculas orgánicas complejas de forma aeróbica, siendo copiótrofo, ya que tiende a incrementar su abundancia en el suelo después de que se incorpora carbono ( Fierer, Bradford y Jackson, 2007; Eilers, Lauber, Knight y Fierer, 2010) y después de incrementar el pH del suelo ( Lauber, Hamady, Knight y Fierer, 2009) obteniendo el décimo lugar en el presente estudio. Aunque Bacillus perteneciente a Firmicutes, es una rizobacteria solubilizadora de potasio o BPCV ( Etesami et al., 2017 ) en el presente estudio se registró una abundancia baja.
El análisis de similitud porcentual (SIMPER) realizado para cuantificar la contribución de los taxa en términos de abundancia relativa y las diferencias observadas con el índice de Bray-Curtis se presentan en el Cuadro 2. Solo se incluyen las rizobacterias que obtuvieron un promedio de disimilitud > 0.10 y que obtuvieron un valor P < 0.05, explicando la mayor parte de las diferencias.
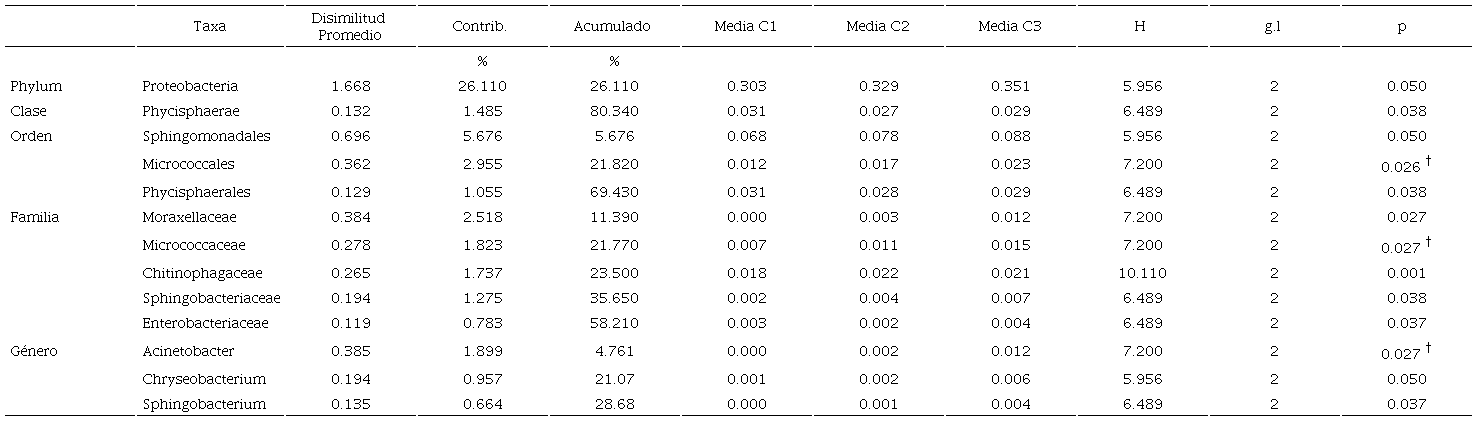
Contrib. % = porcentaje de contribución; H = valor Kruskal-Wallis; g.l. = grados de libertad; P = valor de significancia; †bacteria promotora del crecimiento vegetal. Contrib. % = contribution percentage; H = Kruskal-Wallis value; g.l. = degrees of freedom; p = significance value; †plant growth promoting bacteria.
Entre las abundancias relativas de las razas estudiadas, Sphingomonadales miembro de Proteobacteria, y Chryseobacterium perteneciente al phylum Flavobacteria no registraron diferencia significativa ( P < 0.05); Cuadro 2. Por el contrario, los taxa que presentaron diferencia significativa se describen a continuación: Enterobacteriaceae miembro de Proteobacteria; los miembros de Enterobacteriaceae se pueden encontrar en suelo, granos y plantas, muchas de sus especies causan tizón, marchitez y podredumbre blanda en el maíz, a menudo destruyendo cantidades sustanciales de la pared celular vegetal de las plantas ( Brenner et al., 2005 ), obteniendo en abundancia de 0.2% entre las tres razas; Acinetobacter es miembro de la familia Moraxellaceae que suele encontrarse de forma natural en los suelos ( Brenner et al., 2005 ); es un género BPCV que promueve el crecimiento vegetal produciendo fitohormonas, sideróforos y solubilizando el fosfato tricálcico insoluble ( Sachdev, Nema, Dhakephalkar, Zinjarde y Chopade, 2010).
El orden Phycisphaerales es miembro de la clase Phycisphaera, phylum Planctomycetes; este último suele ser afectado por la distribución de oxígeno en el suelo ya que su abundancia es menor en el suelo cercano a la rizósfera óxica que en el suelo anóxico ( Derakshani, Lukow y Liesack, 2001) registrando un 5% de abundancia en el presente estudio. La familia Micrococcaceae pertenece al orden Micrococcales y al phylum Actinobacteria, el cual se caracteriza por ser BPCV, capaz de inhibir patógenos, sintetizar sustancias reguladoras del desarrollo vegetal y la disponibilidad de minerales y nutrientes ( Franco-Correa y Cahavarro, 2016).
El género Sphingobacterium pertenece a la familia Sphingobacteriaceae; este género, en determinados cultivos de gramíneas, atenúa la respuesta al estrés por sequía ( Khan, Glielich, Phan, Redman y Doty, 2012; Comas, Becker, Cruz, Byrne y Dierig, 2013); algunas de sus especies tienen aptitudes para incrementar el crecimiento, además de que se han aislado de las raíces del maíz ( Mehnaz, Weselowski y Lazarovits, 2007). Proteobacteria es uno de los phylum que suele ser predominante en la rizósfera de maíz; es de crecimiento rápido, ya que participa en la liberación del carbono lábil; no obstante, en los suelos no rizosféricos suele enriquecerse con los microbios oligotróficos de crecimiento lento, tales como Planctomycetes, Actidobacteria y Chlorofexi. En estudios previos se ha demostrado que las diversidades microbianas contribuyen a la funcionalidad del maíz ( Mehta et al., 2021 ). La familia Chitinophagaceae es miembro de Bacteroidetes, phylum involucrado en la degradación de moléculas orgánicas; en el suelo degradan material vegetal y su abundancia relativa aumenta con la adición de carbono en la rizósfera ( Fierer et al., 2007 ; Eilers et al., 2010 ).
En el Cuadro 3 se muestran los rendimientos en peso de grano y peso seco de cada raza de maíz criollo junto con una estimación aproximada en mega gramos por hectárea. Asimismo, se presentan los resultados del peso de grano evaluado con respecto a la selección de las 10 mejores mazorcas de cada tratamiento, el peso seco calculado (considerando tres plantas por tratamiento) y la estimación muestran también.

PG†: peso promedio de 10 mazorcas; PS = peso seco de plantas. PG†: mean weight of 10 corncobs; PS = dry weight of plants.
La comparación múltiple de medias respecto a los datos obtenidos del peso de grano dio como resultado una diferencia notable entre la media del C2, destinado para grano, contra el resto de las razas. De acuerdo con los resultados de la estimación de producción en peso seco por hectárea, el C2 presentó la mayor cantidad en toneladas con respecto a las otras dos razas de maíz, mientras que los criollos 1 y 3 no presentaron una diferencia significativa entre ambas. En cuanto al peso seco estimado por hectárea, el C2 obtuvo la mayor producción (10.61 Mg ha -1), de la misma forma para el rendimiento en grano (15.56 Mg ha -1) con respecto a las otras dos razas ( Cuadro 3).
Conclusiones
Entre las tres razas de maíz criollo, el C3, destinado para grano, registro la mayor abundancia relativa entre las bacterias con capacidad BPCV (Orden Micrococcales, Familia Micrococcales, género Acinetobacter y Sphingobacterium) que demostraron tener un promedio de disimilitud > 0.10 y un valor P < 0.05 en la prueba de Kruskal-Wallis, con una correlación positiva con el rendimiento de los cultivos. Por tanto, el genotipo de la raza C2 cumple funciones de doble propósito (grano y forraje) y puede ser considerado como candidato para preservar y evaluar, bajo condiciones diferentes, su rendimiento en grano; de igual manera C2 fue la raza criolla con mayor rendimiento estimado en el presente estudio con 15.57 toneladas por hectárea.
Declaración de Ética
No aplicable. En virtud de que no se utilizó ningún agente químico que pudiera dañar el ambiente del suelo, ni organismos transgénicos. Se cumple con las normas establecidas por Terra Latinoamericana.
Consentimiento para Publicación
Todos los autores han leído y aprobado el manuscrito final y han dado su consentimiento para su publicación.
Disponibilidad de Datos
No aplicable.
Conflicto de Intereses
Los autores declaran que no tienen intereses en competencia.
Financiación
No aplicable.
Contribución de los Autores
Conceptualización de la investigación, diseño metodológico de la misma e interpretación de datos, redacción y revisión de manuscrito: J.V.A. Realización de trabajo experimental, análisis metodológico metagenómico, revisión y redacción de artículo: M.L.A. Trabajo de campo y rendimientos en grano de las razas de maíz: Y.D.C. Análisis metodológico metagenómico, revisión y redacción de artículo: E.M.M.M. Diseño, análisis de los resultados y la revisión del manuscrito: E.B.C., G.Z.C., y A.C.M. Revisión de datos y manuscrito: R.R.G.E. Revisión, supervisión de avances del proyecto, redacción y responsable de la publicación del manuscrito: A.M.R. Conceptualización de la investigación, diseño metodológico, análisis metagenómico, revisión de manuscrito: C.G.P.
Agradecimientos
Se agradece a la Universidad Autónoma Agraria Antonio Narro por el apoyo financiero del que se derivó el presente estudio, con clave de proyecto: 38111-425609002-2823.
References
AbdElgawad, H., Abuelsoud, W., Madany, M. M. Y., Selim, S., Zinta, G., Mousa, A. S. M., & Hozzein, W. N. (2020). Actinomycetes Enrich Soil Rhizosphere and Improve Seed Quality as well as Productivity of Legumes by Boosting Nitrogen Availability and Metabolism. Biomolecules, 10(12), 1-19. https://doi.org/10.3390/biom10121675
Acosta-Martínez, V., Dowd, S., Sun, Y., & Allen, V. (2008). Tag-encoded pyrosequencing analysis of bacterial diversity in a single soil type as affected by management and land use. Soil Biology and Biochemistry, 40(11), 2762-2770. https://doi.org/10.1016/j.soilbio.2008.07.022
Ahmed, V., Verma, M. K., Gupta, S., Mandhan, V., & Chauhan, N. S. (2018). Metagenomic profiling of soil microbes to mine salt stress tolerance genes. Frontiers in Microbiology, 9, 1-11.
Aira, M., Gómez-Brandón, M., Lazcano, C., Bååth, E., & Domínguez, J. (2010). Plant genotype strongly modifies the structure and growth of maize rhizosphere microbial communities. Soil Biology and Biochemistry, 42(12), 2276-2281. https://doi.org/10.1016/j.soilbio.2010.08.029
Akhtar, N, Qureshi, M. A., Iqbal, A., Ahmad, M. J., & Khan, K. H. (2012). Influence of Azotobacter and IAA on symbiotic performance of Rhizobium and yield parameters of lentil. Journal of Agricultural Research, 50, 361-372.
Beals, E. W. (1984). Bray-Curtis ordination: an effective strategy for analysis of multivariate ecological data. In A. MacFadyen, & E. D. Ford (Eds.). Advances in Ecological Research (pp. 1-55). Cambridge, MA, USA: Academic Press. https://doi.org/10.1016/S0065-2504(08)60168-3
Brenner, D. J., Krieg, N. R., Staley, J. T., Garrity, G. M., Boone, D. R., De Vos, P., … & Schleifer, K. H. (2005). Bergey’s Manual of Systematic Bacteriology. New York, NY, USA: Springer. https://doi.org/10.1007/0-387-28022-7
Caporaso, J. G., Kuczynski, J., Stombaugh, J., Bittinger, K., Bushman, F. D., Costello, E. K., … & Knight, R. (2010). QIIME allows analysis of high-throughput community sequencing data. Nature Methods, 7(5), 335-336. https://doi.org/10.1038/nmeth.f.303
Cary, S. C., McDonald, I. R., Barrett, J. E., & Cowan, D. A. (2010). On the rocks: The microbiology of antarctic dry valley soils. Nature Reviews Microbiology, 8(2), 129-138. https://doi.org/10.1038/nrmicro2281
Chagas, F. O., Pessotti, R. C., Caraballo-Rodríguez, A. M., & Pupo, M. T., (2018). Chemical signaling involved in plant-microbe interactions. Chemical Society Reviews, 47(5), 1652-1704. https://doi.org/10.1039/c7cs00343a
Chaudhry, V., Rehman, A., Mishra, A., Chauhan, P. S., & Nautiyal, C. S. (2012). Changes in bacterial community structure of agricultural land due to long-term organic and chemical amendments. Microbial Ecology, 64, 450-460. https://doi.org/10.1007/s00248-012-0025-y
Chukwuneme, C. F., Babalola, O. O., Kutu, F. R., & Ojuederie, O. B. (2020). Characterization of actinomycetes isolates for plant growth promoting traits and their effects on drought tolerance in maize. Journal of Plant Interactions, 15(1), 93-105. https://doi.org/10.1080/17429145.2020.1752833
Coates, J. D., Cole, K. A., Chakraborty, R., O’Connor, S. M., & Achenbach, L. A. (2002). Diversity and ubiquity of bacteria capable of utilizing humic substances as electron donors for anaerobic respiration. Applied and Environmental Microbiology, 68(5), 2445-2452. https://doi.org/10.1128/AEM.68.5.2445-2452.2002
Comas, L. H., Becker, S., Cruz, V. M., Byrne, P. F., & Dierig, D. A. (2013). Root traits contributing to plant productivity under drought. Frontiers in Plant Science, 4, 1-16. https://doi.org/10.3389/fpls.2013.00442
CONABIO (Comisión Nacional para el Conocimiento y Uso de la Biodiversidad). (2020). Razas de maíz de México. Consultado el 28 de septiembre, 2022, desde Consultado el 28 de septiembre, 2022, desde https://www.biodiversidad.gob.mx/diversidad/alimentos/maices/razas-de-maiz
Cregger, M. A., Veach, A. M., Yang, Z. K., Crouch, M. J., Vilgalys, R., Tuskan, G. A., & Schadt, C. W. (2018). The populus holobiont: Dissecting the effects of plant niches and genotype on the microbiome. Microbiome, 6, 1-14. https://doi.org/10.1186/s40168-018-0413-8
Delgado-Baquerizo, M., Oliverio, A. M., Brewer, T. E., Benavent-González, A., Eldridge, D. J., Bardgett, R. D., … & Fierer, N. (2018). A global atlas of the dominant bacteria found in soil. Science, 359(6373), 320-325. https://doi.org/10.1126/science.aap9516
Derakshani, M., Lukow, T., & Liesack, W. (2001). Novel bacterial lineages at the (sub)division level as detected by signature nucleotide-targeted recovery of 16S rRNA genes from bulk soil and rice roots of flooded rice microcosms. Applied and Environmental Microbiology, 67(2), 623-631. https://doi.org/10.1128/AEM.67.2.623-631.2001
Dimitriu, P. A., & Grayston, S. J. (2010). Relationship between soil properties and patterns of bacterial β-diversity across reclaimed and natural boreal forest soils. Microbial Ecology, 59(3), 563-573. https://doi.org/10.1007/s00248-009-9590-0
Edgar, R. C. (2010). Search and clustering orders of magnitude faster than BLAST. Bioinformatics, 26, 2460-2461. https://doi.org/10.1093/bioinformatics/btq461
Edwards, C. (1993). Isolation properties and potential applications of thermophilic actinomycetes. Applied Biochemistry Biotechnology, 42, 161-179. https://doi.org/10.1007/BF02788050
Eilers, K. G., Lauber, C., Knight, R., &Fierer, N. (2010). Shifts in bacterial community structure associated with inputs of low molecular weight carbon compounds to soil. Soil Biology and Biochemistry, 42(6), 896-903. https://doi.org/10.1016/j.soilbio.2010.02.003
Etesami, H., Emami, S., & Alikhani, H. A. (2017). Potassium solubilizing bacteria (KSB): Mechanisms, promotion of plant growth, and future prospects, A review. Journal of Soil Science and Plant Nutrition, 17(4), 897-911. https://doi.org/10.4067/S0718-95162017000400005
FAOSTAT (Food and Agriculture Organization Corporate Statistical Database). (2021). Production/Yield quantities of maize (corn) in world + (total) 2021. Consultado 12 de marzo, 2023, desde Consultado 12 de marzo, 2023, desde https://www.fao.org/faostat/es/#data/QCL
Fierer, N., Bradford, M. A., & Jackson, R. B. (2007). Toward an ecological classification of soil bacteria. Ecology, 88(6), 1354-1364. https://doi.org/10.1890/05-1839
Franco-Correa, M., & Chavarro-Anzola, V. (2016). Actinobacteria as plant growth-promoting rhizobacteria. In D. Dhanasekaran, & Y. Jiang (Eds.). Actinobacteria (pp. 249-270). London: United Kingdom: InTechOpen. https://doi.org/10.5772/61291
García-De la Peña, C., Rojas-Domínguez, M., Ramírez-Bautista, A., Vaca-Paniagua, F., Díaz-Velásquez, C., Ávila-Rodríguez, V., … & Meza-Herrera, C. A. (2019). Microbiota bacteriana oral de la tortuga del bolsón Gopherus flavomarginatus en la Reserva de la Biosfera Mapimí, México. Revista Mexicana de Biodiversidad, 90, 1-14. https://doi.org/10.22201/ib.20078706e.2019.90.2683
González, F. H., & Fuentes, M. N. (2017). Mecanismo de acción de cinco microorganismos promotores de crecimiento vegetal. Revista de Ciencias Agrícolas, 34(1), 17-31. https://doi.org/10.22267/rcia.173401.61
Guillén-Pérez, L. A., Sánchez-Quintanar, C., Mercado-Domenech, S., & Navarro-Garza, H. (2002). Análisis de atribución causal en el uso de semilla criolla y semilla mejorada de maíz. Agrociencia, 36(3), 377-387.
Hammer, O., Harper, D. A. T., & Ryan, P. D. (2001). PAST: Paleontological statistics software package for education and data analysis. Palaeontologia Electronica, 4, 1-9.
He, W. J., Zhang, L., Yi, S. Y., Tang, X. L., Yuan, Q. S., Guo, M. W., ... & Liao, Y. C. (2017). An aldo-keto reductase is responsible for Fusarium toxin-degrading activity in a soil Sphingomonas strain. Scientific Reports, 7(1), 9549. https://doi.org/10.1038/s41598-017-08799-w
Illumina (2021a). 16S Metagenomic sequencing library preparation, preparing 16S ribosomal RNA gene amplicons for the Illumina MiSeq system. Consultada el 29 de septiembre, 2021, desde: Consultada el 29 de septiembre, 2021, desde: https://support.illumina.com/documents/documentation/chemistry_documentation/16s/16s-metagenomic-library-prep-guide-15044223-b.pdf
Illumina (2021b). Nextera XT DNA library prep kit reference guide. Consultada el 29 de septiembre, 2021, desde: Consultada el 29 de septiembre, 2021, desde: https://support.illumina.com/content/dam/illumina-support/documents/documentation/chemistry_documentation/samplepreps_nextera/nexteradna/nextera-dna-library-prep-reference-guide-15027987-01.pdf
Itävaara, M., Salavirta, H., Marjamaa, K., & Ruskeeniemi, T. (2016). Geomicrobiology and metagenomics of terrestrial deep subsurface microbiomes. Advances in Applied Microbiology, 94, 1-77. https://doi.org/10.1016/bs.aambs.2015.12.001
Janssen, P. H. (2006). Identifying the dominant soil bacterial taxa in libraries of 16S rRNA and 16S rRNA genes. Applied and Environmental Microbiology, 72(3), 1719-1728. https://doi.org/10.1128/AEM.72.3.1719-1728.2006
Jones, R. T., Robeson, M. S., Lauber, C. L., Hamady, M., Knight, R ., &Fierer, N. (2009). A comprehensive survey of soil acidobacterial diversity using pyrosequencing and clone library analyses. The ISME Journal, 3(4), 442-453. https://doi.org/10.1038/ismej.2008.127
Karnwal, A. (2022). A comparative study of native growth-promoting rhizobacteria and commercial biofertilizer on maize ( Zea mays L.) and wheat ( Triticum aestivum L.) development in a saline environment. Journal of Plant Protection Research, 62(1), 49-57.
Keum, Y. S., Lee, Y. J., & Kim, J. H. (2008). Metabolism of nitrodiphenyl ether herbicides by dioxin-degrading bacterium Sphingomonas wittichii RW1. Journal of Agricultural and Food Chemistry, 56(19), 9146-9151. https://doi.org/10.1021/jf801362k
Khan, Z., Glielich, G., Phan, H., Redman, R., & Doty, S. (2012). Bacterial and yeast endophytes from poplar and willow promote growth in crop plants and grasses. International Scholarly Research Notices, 2012, 1-12. https://doi.org/10.5402/2012/890280
Kim, J. S., Dungan, R. S., & Crowley, D. (2008). Microarray analysis of bacterial diversity and distribution in aggregates from a desert agricultural soil. Biology and Fertility of Soils, 44, 1003-1011. https://doi.org/10.1007/s00374-008-0291-5
Klindworth, A., Pruesse, E., Schweer, T., Peplies, J., Quast, C., Horn, M., & Glöckner, F. O. (2012). Evaluation of general 16S ribosomal RNA gene PCR primers for classical and next-generation sequencing-based diversity studies. Nucleic Acids Research, 41(1), 1-11. https://doi.org/10.1093/nar/gks808
Kovaleva, O. l., Elcheninov, A. G., Kublanov, I. V., & Bonch-Osmolovskaya, E. (2019). Tepidisphaeraceae. In W. B. Whitman (Ed.). Bergey’s manual of systematics of archaea and bacteria (pp. 549-555). Hoboken, NJ, USA: John Wiley & Sons. https://doi.org/10.1002/9781118960608.obm00143
Lauber, C. L., Hamady, M., Knight, R., &Fierer, N . (2009). Pyrosequencing-based assessment of soil pH as a predictor of soil bacterial community structure at the continental scale. Applied and Environmental Microbiology, 75(15), 5111-5120. https://doi.org/10.1128/AEM.00335-09
Lladó, S., Žifčáková, L., Větrovský, T., Eichlerová, I., & Baldrian, P. (2016). Functional screening of abundant bacteria from acidic forest soil indicates the metabolic potential of Acidobacteria subdivision 1 for polysaccharide decomposition. Biology and fertility of soils, 52, 251-260. https://doi.org/10.1007/s00374-015-1072-6
Manickam, N., Reddy, M. K., Saini, H. S., & Shanker, R. (2008). Isolation of hexachlorocyclohexane-degrading Sphingomonas sp. by dehalogenase assay and characterization of genes involved in gamma-HCH degradation. Journal of Applied Microbiology, 104(4), 952-960. https://doi.org/10.1111/j.1365-2672.2007.03610.x
Männistö, M. K., Tiirola, M., & Häggblom, M. M. (2007). Bacterial communities in Arctic fjelds of Finnish Lapland are stable but highly pH-dependent. FEMS Microbiology Ecology, 59(2), 452-465. https://doi.org/10.1111/j.1574-6941.2006.00232.x
Marchesi, J. R., & Ravel, J. (2015). The vocabulary of microbiome research: A proposal. Microbiome, 3(1), 1-3. https://doi.org/10.1186/s40168-015-0094-5
McDonald, D., Price, M. N., Goodrich, J., Nawrocki, E. P., DeSantis, T. Z., Probst, A., … & Hugenholtz, P. (2012). An improved Greengenes taxonomy with explicit ranks for ecological and evolutionary analyses of bacteria and archaea. The ISME Journal, 6, 610-618. https://doi.org/10.1038/ismej.2011.139
Mehnaz, S., Weselowski, B., & Lazarovits, G. (2007). Sphingobacterium canadense sp. Nov., an isolate from corn roots. Systematic and Applied Microbiology, 30(7), 519-524. https://doi.org/10.1016/j.syapm.2007.06.002
Mehta, S., Singh, B., Patra, A., Tripathi, A., Easwaran, M., Choudhary, J. R., … & Aggarwal, S. K. (2021). In M. K. Solanki, P. L. Kashyap, R. A. Ansari, & B. Kumari (Eds.). Maize microbiome: Current insights for the sustainable agriculture. Microbiomes and Plant Health (pp. 267-297). Cambridge, MA, USA: Academic Press. https://doi.org/10.1016/B978-0-12-819715-8.00009-4
Montemayor-Trejo, J. A., Lara-Míreles, J. L., Woo-Reza, J. L., Munguía-López, J., Rivera-González, M., & Trucíos-Caciano, R. (2012). Producción de maíz forrajero ( Zea mays L.) en tres sistemas de irrigación en la Comarca Lagunera de Coahuila y Durango, México. Agrociencia, 46(3), 267-278.
Mujakic, I., Piwosz, K., & Koblizek, M. (2022). Phylum Gemmatimonadota and its role in the environment. Microorganisms, 10(1), 1-17. https://doi.org/10.3390/microorganisms10010151
Navarro-Garza, H., Hernández-Flores, M., Castillo-González, F., & Pérez-Olvera, M. A. (2012). Diversidad y caracterización de maíces criollos: Estudio de caso en sistemas de cultivo en la Costa Chica de Guerrero, México. Agricultura, Sociedad y Desarrollo, 9(2), 149-165.
Navas-Molina, J. A., Peralta-Sánchez, J. M., González, A., McMurdie, P. J., Vázquez-Baeza, Y., Xu, Z., … &Knight, R . (2013). Advancing our understanding of the human microbiome using QIIME. Methods in Enzymology, 531, 371-444. https://doi.org/10.1016/B978-0-12-407863-5.00019-8
Nazir, N., Kamili, A. N., Zargar, M. Y., Khan, I., Shah, D., Parray, J. A., & Tyub, S. (2016). Effect of Root Exudates on Rhizosphere Soil Microbial Communities. Journal of Research and Develodment, 16, 88-95.
Neilson, J. W., Califf, K., Cardona, C., Copeland, A., van Treuren, W., Josephson, K. L., … & Maier, R. M. (2017). Significant Impacts of Increasing Aridity on the Arid Soil Microbiome. mSystems, 2(3). https://doi.org/10.1128/mSystems.00195-16
Nemergut, D. R., Costello, E. K., Hamady, M. , Lozupone, C., Jiang, L., Schmidt, S. K., … &Knight, R . (2011). Global patterns in the biogeography of bacterial taxa. Environmental Microbiology, 13(1), 135-144. https://doi.org/10.1111/j.1462-2920.2010.02315.x
Odelade, K. A., & Babalola, O. O. (2019). Bacteria, fungi and archaea domains in rhizospheric soil and their effects in enhancing agricultural productivity. International Journal of Environmental Research and Public Health, 16(20), 1-19. https://doi.org/10.3390/ijerph16203873
Peiffer, J. A., Spor, A., Koren, O., Jin, Z., Tringe, S. G., Dangl, J. L., … & Ley, R. E. (2013a). Diversity and heritability of the maize rhizosphere microbiome under field conditions. Proceedings of the National Academy of Sciences of the United States of America, 110(16), 6548-6553. https://doi.org/10.1073/pnas.1302837110
Peiffer, J. A. , &Ley, R. E. (2013b). Exploring the maize rhizosphere microbiome in the field: A glimpse into a highly complex system. Communicative & integrative biology, 6(5), e25177. https://doi.org/10.4161/cib.25177
Peng, R. H., Xiong, A. S., Xue, Y., Fu, X. Y., Gao, F., Zhao, W., … & Yao, Q. H. (2008). Microbial biodegradation of polyaromatic hydrocarbons. FEMS Microbiology Reviews, 32(6), 927-955. https://doi.org/10.1111/j.1574-6976.2008.00127.x
Qaisrani, M. M., Zaheer, A., Mirza, M. S., Naqqash, T., Qaisrani, T. B., Hanif, M. K., … & Rasool, M. (2019). A comparative study of bacterial diversity based on culturable and culture-independent techniques in the rhizosphere of maize ( Zea mays L)Saudi Journal of Biological Sciences, 26(7), 1344-1351. https://doi.org/10.1016/j.sjbs.2019.03.010
Rajakaruna, N., & Boyd, R. S. (2008). Edaphic Factor. In S. E. Jørgensen, & B. D. Fath (Eds.). Encyclopedia of Ecology (pp. 1201-1207). Cambridge, MA, USA: Academic Press. https://doi.org/10.1016/B978-008045405-4.00484-5
Ravanbakhsh, M., Kowalchuk, G. A., & Jousset, A. (2020). Targeted plant hologenome editing for plant trait enhancement. New Phytologist, 229, 1067-1077. https://doi.org/10.1111/nph.16867
Raza, W., Ling, N., Yang, L., Huang, Q., & Shen, Q. (2016). Response of tomato wilt pathogen Ralstonia solanacearum to the volatile organic compounds produced by a biocontrol strain Bacillus amyloliquefaciens SQR-9. Scientific Reports, 6(1), 1-13. https://doi.org/10.1038/srep24856
Sachdev, D., Nema, P., Dhakephalkar, P., Zinjarde, S., & Chopade, B. (2010). Assessment of 16S rRNA gene-based phylogenetic diversity and promising plant growth-promoting traits of Acinetobacter community from the rhizosphere of wheat. Microbiological Research, 165(8), 627-638. https://doi.org/10.1016/j.micres.2009.12.002
SADER. (2021). Estimación agricultura crecimiento de 2.6 por ciento en la producción de maíz grano en año agrícola 2021. Consultado el 29 de septiembre, 2022, desde Consultado el 29 de septiembre, 2022, desde https://www.gob.mx/agricultura/prensa/estima-agricultura-crecimiento-de-2-6-por-ciento-en-la-produccion-de-maiz-grano-en-ano-agricola-2021?idiom=es#:~:text=La%20Secretar%C3%ADa%20de%20Agricultura%20y%20Desarrollo%20Rural%20inform%C3%B3%20que%20se,millones%20427%20mil%20436%20toneladas
Sánchez, J. J., Goodman, M. M., & Stuber, C. W. (2000). Isozymatic and morphological diversity in the races of maize of Mexico. Economic Botany, 54(1), 43-59.
Sánchez-Hernández, E., De la Cruz-Lazaro, E., & Sánchez-Hernández, R. (2014). Productividad y caracterización varietal de maíces nativos ( Zea mays L.) colectados en Tabasco, México. Acta Agrícola y Pecuaria, 1(1), 7-15.
Santos-Medellin, C., Edwards, J., Liechty, Z., Nguyen, B., & Sundaresan, V. (2017). Drought Stress Results in a Compartment-Specific Restructuring of the Rice Root-Associated Microbiomes. MBio, 8(4), e00764-17. https://doi.org/10.1128/mBio.00764-17
SAGARPA (Secretaria de Agricultura, Ganadería, Desarrollo Rural, Pesca y Alimentación). (2017). Agrícola Nacional. Planeación Agrícola Nacional 2017-2030. Consultada el 29 de septiembre, 2022, desde: Consultada el 29 de septiembre, 2022, desde: https://www.gob.mx/cms/uploads/attachment/file/255625/Planeaci_n_Agr_cola_Nacional_2017-2030-_parte_dos.pdf.
Singh, C., Singh, P., & Singh, R. (2020). Modern techniques of raising field crops (3 th Ed.). New Delhi, India: Oxford & IBH Pblishing Co. ISBN: 9389688493
Sun, J. G. Zhang, Y. C., Xu, J. & Hu, H. Y. (2010). Isolation, identification and inoculation effect of nitrogen-fixing bacteria “ Sphingomonas GD542” from maize rhizosphere, Chinese Journal of Eco-Agriculture, 18(1), 89-93. https://doi.org/10.3724/SP.J.1011.2010.00089.
Turiján-Altamirano, T., Damián-Huato, M. Á., Ramírez-Valverde, B., Juárez-Sánchez, J. P., & Estrella-Chulín, N. (2012). Manejo tradicional e innovación tecnológica en cultivo de maíz en San José Chiapa, Puebla. Revista Mexicana de Ciencias Agrícolas, 3(6), 1085-1100.
Turrent, F. A., Wise, T. A., & Garvey, E. (2012). Factibilidad de alcanzar el potencial productivo de maíz de México. Consultado el 29 de septiembre, 2022, desde Consultado el 29 de septiembre, 2022, desde https://www.bu.edu/eci/files/2019/06/12-03TurrentMexMaizeSpan.pdf
Vázquez-Baeza, Y., Pirrung, M., Gonzalez, A., & Knight, R . (2013). EMPeror: A tool for visualizing high-throughput microbial community data. GigaScience, 2(1), 1-4. https://doi.org/10.1186/2047-217X-2-16
Vázquez-Carrillo, M. G., Pérez-Camarillo, J. P., Hernández-Casillas, J. M., Marrufo-Diaz, M. L., & Martínez-Ruiz, E. (2010). Calidad de grano y de tortillas de maíces criollos del altiplano y valle del mezquital, México. Revista Fitotecnia Mexicana, 33, 49-56.
Wei, Z., Hu, X., Li, X., Zhang, Y., Jiang, L. , Li, J., … & Liao, X. (2017). The rhizospheric microbial community structure and diversity of deciduous and evergreen forests in Taihu Lake area, China. PLOS ONE, 12(4), 1-22. https://doi.org/10.1371/journal.pone.0174411
Weiss, S., Xu, Z. Z., Peddada, S., Amir, A., Bittinger, K., Gonzalez, A., … &Knight, R. (2017). Normalization and microbial differential abundance strategies depend upon data characteristics. Microbiome, 5, 1-18. https://doi.org/10.1186/s40168-017-0237-y
Yadav, A. N., Verma, P., Kumar, S., Kumar, V., Kumar, M., Sugitha, T. C. K., … & Dhaliwal, H. (2018). Chapter 2 - Actinobacteria from Rhizosphere: Molecular Diversity, Distributions, and Potential Biotechnological Applications. In B. P. Singh, V. K. Gupta, & A. K. Passari (Eds.). New and Future Developments in Microbial Biotechnology and Bioengineering (pp. 13-41). Amsterdam, The Netherlands: Elsevier. https://doi.org/10.1016/B978-0-444-63994-3.00002-3
Yoon, S. H., Ha, S. M., Kwon, S., Lim, J., Kim, Y., Seo, H., & Chun, J. (2017). Introducing EzBioCloud: A taxonomically united database of 16S rRNA gene sequences and whole-genome assemblies. International Journal of Systematic and Evolutionary Microbiology, 67(5), 1613-1617. https://doi.org/10.1099/ijsem.0.001755
Zhang, J., Kobert, K., Flouri, T., & Stamatakis, A. (2014). PEAR: A fast and accurate Illumina Paired-End reAd mergeR. Bioinformatics, 30(5), 614-620. https://doi.org/10.1093/bioinformatics/btt593
Zhao, S., Liu, J., Banerjee, S., Zhou, N., Zhao, Z., Zhang, K., … & Tian, C. (2020). Biogeographical distribution of bacterial communities in saline agricultural soil. Geoderma, 361, 114095. https://doi.org/10.1016/j.geoderma.2019.114095
Zimmermann, J., Gonzalez, J. M., & Saiz-Jimenez, C. (2006). Epilithic biofilms in Saint Callixtus Catacombs (Rome) harbour a broad spectrum of Acidobacteria. Antonie van Leeuwenhoek, 89, 203-208. https://doi.org/10.1007/s10482-005-9020-3
Notas
Notas de autor
‡ Autor para correspondencia: alejamorsa@yahoo.com.mx, cristina.garcia@ujed.mx
