Resumen: La leptospirosis es una zoonosis mundial y es endémica en muchos países. Esta enfermedad se mantiene en la naturaleza por la infección renal crónica de los animales portadores; los roedores y otros mamíferos pequeños son los reservorios más importantes. Además, otras fuentes importantes de infección para el humano son los animales domésticos, como el ganado y los perros. El jabalí (Sus scrofa) es una especie introducida de Europa que está muy extendida en América y particularmente en el centro y sur de Argentina. Esta especie es muy valorada por los cazadores de la región y su carne se consume con mayor frecuencia. En muchos países del mundo (Europa, EE. UU. y Australia) se han realizado estudios sobre seroprevalencia, la seroreactividad no significa que el jabalí manifieste síntomas clínicos de leptospirosis o que los jabalíes sean reservorios de este patógeno bacteriano. Sin embargo, estos animales han estado en contacto con leptospiras en su entorno en el pasado. Este estudio tiene el objetivo de tipificar molecularmente la cepa aislada obtenida a partir de 4 fetos de jabalíes (Sus scrofa) provenientes de la Patagonia argentina. Se realizaron necropsias de los 4 fetos y se cultivaron muestras de riñones, hígado, bazo y pulmón en medios Fletcher y EMJH. Además, las muestras de hígado, bazo, pulmón y riñón de los fetos se procesaron y analizaron por inmunofluorescencia directa. Se utilizó el análisis de repeticiones en tándem de número variable de locus múltiple (MLVA) para caracterizar la cepa aislada. El perfil genético de la cepa de leptospira fue idéntica al perfil de Leptospira borgpetersenii serovar Castellonis Castellon 3 perteneciente al serogrupo Ballum. Hasta donde sabemos, este es el primer aislamiento de Leptospira spp. de un feto de jabalí.
Palabras clave: Leptospira spp, jabalí, genotipo, MLVA, Patagonia, Argentina.
Abstract: Leptospirosis is a worldwide zoonose and is endemic in many countries. This disease is maintained in nature by chronic renal infection of carrier animals, being rodents and other small mammals the most important reservoirs. Also, significant sources of human infection are domestic animals, such as livestock and dogs. The wild boar (Sus scrofa) is an introduced species from Europe which is widespread in America and particularly in the Center and South of Argentina. This species is highly valued by hunters in the region and their meat is consumed more often. In many countries of the world (Europe, USA and Australia) studies of seroprevalence have been carried out, the seroreactivity does not mean that the wild boar has clinical symptoms of leptospirosis or that wild boars are maintenance host of this pathogen. However, these animals have been in contact to leptospiras in their environment in the past. This study has the objective to molecularly genotype the pathogenic Leptospira sp. isolated strain obtained from fetuses of wild boars from Patagonia Argentina. Four fetuses were aborted from a wild boar (Sus scrofa) in Patagonia, the southern region of Argentina. Necropsy was performed of the 4 fetuses and samples of kidneys, liver, spleen and lung were cultivated in Fletcher and EMJH mediums. Also, samples of liver, spleen, lung and kidney of fetuses were processed and analyzed by direct immunofluorescence. Multiple Locus Variable number tandem repeats Analysis (MLVA) was used to characterize the isolated strain. The genetic profile of the isolated pathogenic Leptospira sp. strain was identical to the profile of Leptospira borgpetersenii serovar Castellonis Castellon 3, serogroup Ballum. To the best of our knowledge this is the first isolation of Leptospira spp. from a wild boar fetus.
Keywords: Leptospira spp, wild boar, genotype, MLVA, Patagonia, Argentina.
Artículos
Primer aislamiento de Leptospira borgpetersenii de un feto de jabalí (Sus scrofa)
Instituto Nacional de Tecnología Agropecuaria

Esta obra está bajo una Licencia Creative Commons Atribución-NoComercial 4.0 Internacional.
La leptospirosis es la enfermedad zoonótica más extendida en el mundo. Es causada por una bacteria perteneciente al orden de las espiroquetas. Las cepas patógenas del género Leptospira spp. encuentran su nicho ideal para la transmisión en regiones subtropicales y tropicales. No hay datos disponibles sobre la incidencia de leptospirosis en varios países y, además, la enfermedad con frecuencia es subdiagnosticada y subnotificada, en consecuencia es considerada una enfermedad descuidada severamente (Hartskeerl et al., 2011). Las cepas patógenas de leptospira infectan principalmente a los mamíferos, pero también se pueden encontrar en reptiles y anfibios (Levett, 2001, Adler y Peña, 2010). Esta zoonosis se mantiene en la naturaleza por la infección renal crónica de los animales portadores; los roedores y otros mamíferos pequeños son los reservorios más importantes. Además, fuentes importantes de infección humana son el ganado y los animales domésticos, como los perros. En Argentina, esta enfermedad es endémica y aún no se han implementado programas de control o prevención epidemiológica. Hasta la semana epidemiológica 51 del año 2019 se notificaron 2976 casos humanos al Ministerio de Salud Nacional en el país; la región del centro (Buenos Aires, CABA, Córdoba, Entre Ríos y Santa Fe) es la que cuenta con la mayor cantidad de casos notificados (2019) (Ministerio de Salud Nacional, 2019).
Por un lado, en Ellis et al. (1986) se establecieron cerdos domésticos como anfitriones de mantenimiento para el serogrupo Australis y en Jansen et al. (2007) para el serogrupo Pomona. Por otro lado, los jabalíes se clasifican como hospedadores accidentales para el serovar Grippothyphosa en Treml et al. (2003) y en Jansen (et al.) 2007 para el serogrupo Pomona y Bratislava. Slavica et al. (2010) realizaron un estudio serológico en jabalíes en Croacia utilizando MAT, en este estudio los serovares más frecuentes fueron Australis (33,3%), Pomona (21,8%) y Tarassovi (14,3%) de un total de 351 muestras de suero, el título más alto obtenido fue 1/3200 para serovar Pomona. En un estudio serológico reciente de jabalíes (Sus scrofa) en Polonia (Zmudzki et al., 2016) analizaron 3621 muestras de sangre de jabalíes en busca de Leptospira spp. serovars/serogroup: Icterohaemorrhagie, Grippothyphosa, Sejore, Tarassovi, Pomona, Canicola, Bratislava, Autumnalis, Hardjo y Ballum. El serogrupo Ballum no dio títulos en las muestras de suero analizadas . Los serovares Pomona y Sejore se informan como los más comunes en cerdos domésticos en Polonia; sin embargo, (Zmudzki et al., 2016) estos serovares fueron poco frecuentes. En el mismo estudio se menciona el aumento de la población de jabalíes de vida libre en Europa en las zonas urbanas y suburbanas, y la amenaza de una posible diseminación de cepas patógenas de leptospiras es preocupante. La necesidad de controlar la población también constituye un riesgo para los cazadores de infectarse con Leptospira spp. (Richard et al., 2015; Jensen et al., 2007).
Además, la expansión geográfica de los humanos hacia áreas no urbanizadas está causando que los animales silvestres tengan que vivir en las cercanías de los habitantes de estos pueblos y ciudades. En el 2006, relacionaron un caso humano de leptospirosis en Berlín con la posible infección por agua dulce contaminada con orina de jabalí (Jansen et al., 2006). En una revisión de los jabalíes como fuentes de infecciones en humanos y ganado (Meng et al., 2009), solo se enumeran tres estudios de seroreactividad positiva: Alemania (Jansen et al., 2007), California (EE. UU.) (Clark et al., 1983) e Italia (Ebani et al., 2003). En Jansen et al. (2007) las muestras de suero de jabalíes de las zonas urbanas de Berlín fueron analizadas por MAT, los serovares Pomona y Bratislava fueron los más frecuentes, estos resultados y la demostración de que se encontraron leptospiras utilizando la tinción de plata en muestras de riñón de jabalíes indicaron que estos animales son animales de mantenimiento (reservorios) también en áreas urbanas. En Eslovenia (Vengust et al., 2003) en un estudio de seroprevalencia de Leptospira spp. en 437 muestras de suero de jabalí se encontró que la prevalencia de anticuerpos de este estudio fue mayor (45,5%) que la prevalencia determinada en estudios previos: Italia (6%; Ebani et al., 2003), República Checa (16,9%; Treml et al., 2003), Alemania (24%; Schönberg et al., 1999), Polonia (25,2%; Krawczyk, 2000), Croacia (26%; Cvetnic et al., 2003), Austria (30%; Deutz et al., 2002) y Australia (20%; Mason et al., 1998).
En Sudamérica no se han realizado muchos estudios de seroprevalencia en jabalí, sin embargo, en Brasil (2011) se realizó un estudio serológico con MAT en una población cautiva de jabalíes para consumo humano. En este estudio, 63 animales fueron positivos a Leptospira spp., los serovares mejor representados fueron: Hardjo, Copenhageni y Pomona (Fornazari et al., 2011).
Hasta donde sabemos, este es el primer aislamiento de L. borgpetersenii de fetos de jabalíes (Sus scrofa). Existen muchos estudios sobre prevalencia en jabalíes a nivel mundial, sin embargo, aparentemente no existen estudios sobre aislamientos de cepas patógenas en este grupo animal. El objetivo de este trabajo fue aislar y genotipificar la cepa aislada a partir de los fetos recibidos en el laboratorio de Leptospirosis, Centro de referencia de la OIE, perteneciente al Instituto de Patobiología del CICVyA, INTA Castelar.
Aislamiento de Leptospira spp.: se realizaron las necropsias de los 4 fetos, provenientes del parque nacional Nahuel Guapi (Patagonia), utilizando el protocolo descrito por Faine et al. (1999), y se cultivaron las muestras de riñones, hígado, bazo y pulmón en medios Fletcher y EMJH. Los cultivos se incubaron a 28 °C hasta que se determinó el desarrollo, cada 15 días se observaron los cultivos bajo microscopía de campo oscuro.
Inmunofluorescencia: la tinción de inmunofluorescencia directa de las muestras de hígado, bazo, pulmón y riñón se realizó con un conjugado multivalente FA, LEP-FAC (Seasinglab, Argentina) específico para Leptospira spp.
Caracterización molecular: las cepas de referencia y la cepa aislada se cultivaron en medios Fletcher (Laboratorios Difco) a 28 ºC. Para las extracciones de ADN se usó el protocolo utilizado con la resina Chelex-100 (Bio Rad). Se usó el análisis de repeticiones en tándem de número variable de locus múltiples (MLVA) para caracterizar la cepa aislada con 1 conjunto de oligonucleótidos específicos para las cepas patógenas de L. interrogans, L. kirschneri y L. borgpetersenii, se usaron los siguientes loci: VNTRS: 4, 7, 10, Lb4 y Lb5 (Salaün et al., 2006). El volumen final (50 µl) de cada mezcla de reacción contenía PCR Buffer (Tris-HCL 20 mM, pH 8.4; KCl 50 mM), desoxinucleósidos trifosfatos 200 µM, cada cebador correspondiente 2 µM, MgCl2 2 mM, ADN polimerasa Taq 1.25U (Invitrogen) y plantilla de ADN 5 µl. Las PCR se llevaron a cabo en un termociclador Thermo Scientific PxE 0,2 de la siguiente manera: 94 ºC durante 5 minutos, seguido de 35 ciclos de desnaturalización a 94 ºC durante 30 segundos, recocido a 55 ºC durante 30 segundos y extensión a 72 ºC durante 90 segundos, con un ciclo final a 72 ºC durante 10min. Las muestras amplificadas (15 µl) se revelaron mediante electroforesis en un gel de agarosa al 2% en tampón TAE (Tris-acetato 40 mM, EDTA 1 mM) con 0,2 ul µg/ml de bromuro de etidio a 100 V durante 50 minutos. Las bandas de ADN amplificadas se visualizaron tras la exposición a la luz UV (transiluminador Uvi Tec BTS-20.M). Los tamaños de amplicón se estimaron usando CienMarker (Biodynamics) y el programa GelAnalyzer 2010a. Para calcular el número de copias repetidas se utilizó la siguiente fórmula: Número de repeticiones (pb) = [Tamaño de fragmento (pb) - Regiones de flanqueo (pb)] / Tamaño de repetición (pb). Los números de copia repetidos se redondearon a los números enteros más cercanos. Si el número de copia era menor que uno, se redondeó a cero.
La inmunofluorescencia directa fue positiva en el hígado, el bazo y el riñón de los fetos. Se aisló una cepa de Leptospira spp. de riñones e hígado en medio Fletcher después de 47 días de incubación a 28 ºC. El genotipo del aislamiento determinado por MLVA, coincide con el perfil genético de Leptospira borgpetersenii serovar Castellonis Castellon 3 (-, -, 1,4,6) del serogrupo Ballum (figura 1).
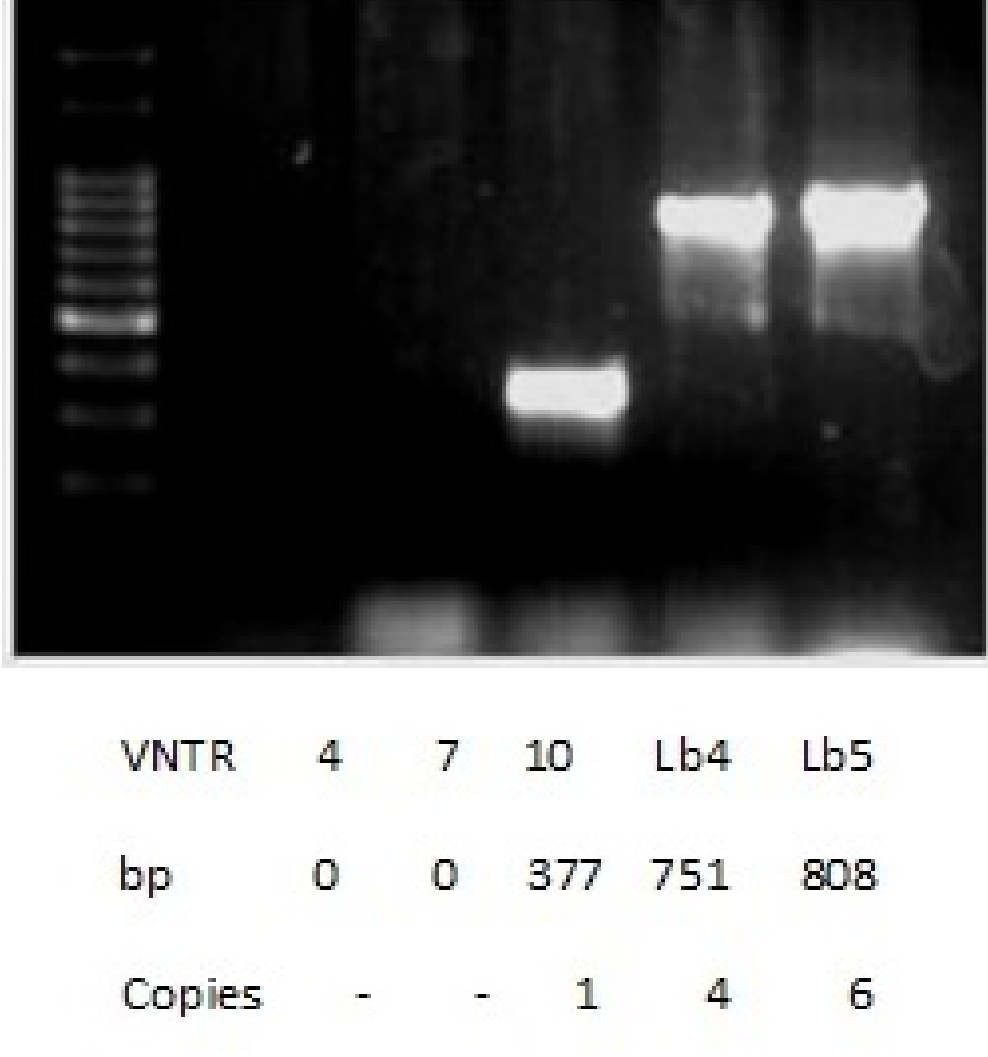
Figura 1
Genotipificación MLVA.
Hasta donde sabemos, esta es la primera cepa de Leptospira borgpetersenii aislada de jabalíes en América del Sur obtenida de fetos abortados (figuras 2 y 3). Este hallazgo sugiere que los jabalíes son susceptibles a L. borgpetersenii serovar Castellonis Castellon 3 del serogrupo Ballum. Este genotipo se caracterizó previamente en poblaciones de ratones en Argentina (Grune et al., 2013). La misma especie L. borgpetersenii se aisló en muestras de agua en un río urbano en Argentina (Francoise et al., 2013) y se aisló en casos clínicos de animales domésticos (Grune et al., 2016) y humanos (Goncalves et al., 2010). Varios estudios sobre seroreactividad realizados en poblaciones de jabalíes (Europa, EE. UU., y Australia) (Clark et al., 1983; Deutz et al., 2002; Ebani et al., 2003; Fornazari et al., 2011; Jansen et al., 2007; Krawczyk et al., 2000; Manson et al., 1998; Meng et al., 2009; Saliki et al., 1998, Schönberg et al., 1999; Slavica et al., 2010; Treml et al., 2003; Vengust et al., 2003; Zwdzki et al., 2016) muestran la exposición en el medioambiente y nichos ecológicos donde viven las poblaciones de jabalíes a cepas leptospiras patógenas. En este estudio se logró aislar una cepa a partir de un feto abortado de Sus scrofa, genotipificada molecularmente empleando MLVA, demostrando la importancia que presentan los animales silvestres en la diseminación de cepas patógenas al medioambiente. Este hallazgo también refleja la posibilidad de infección en jabalíes, ya que la cepa fue aislada en fetos, sin embargo, no se encontraron restos de la madre en el lugar. Es importante profundizar estudios epidemiológicos no solo en jabalíes, sino también en otros animales silvestres y en el medioambiente, para poder conocer la casuística actual presente en el país y así poder tomar medidas de prevención en las zonas de mayor riesgo de contagio.
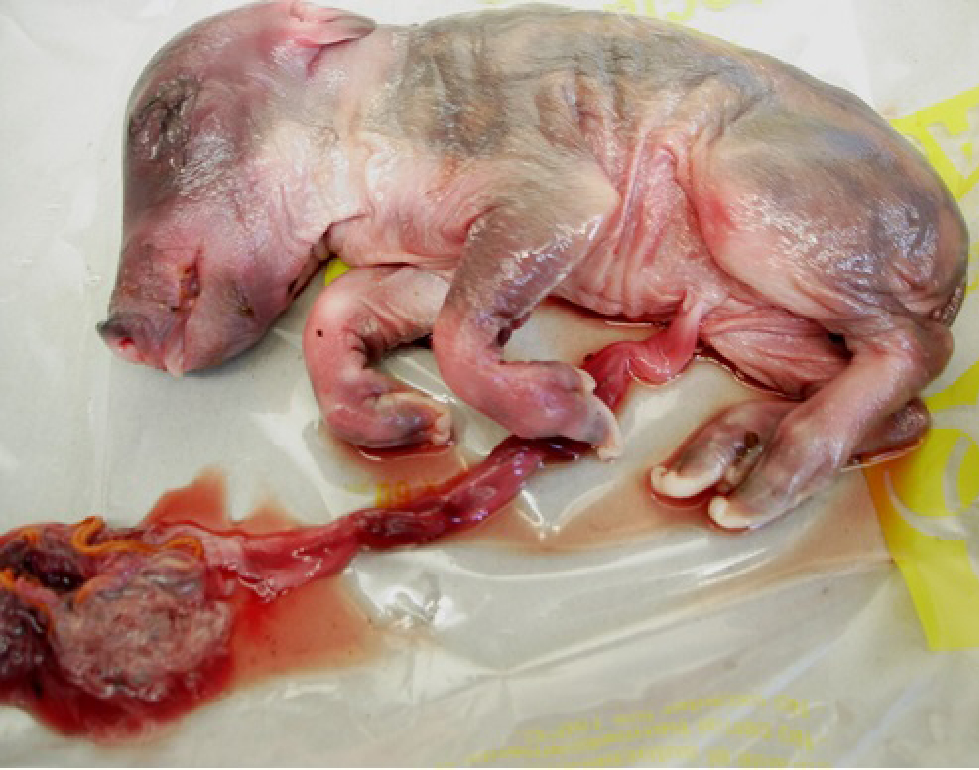
Figura 2
Feto jabalí abortado.
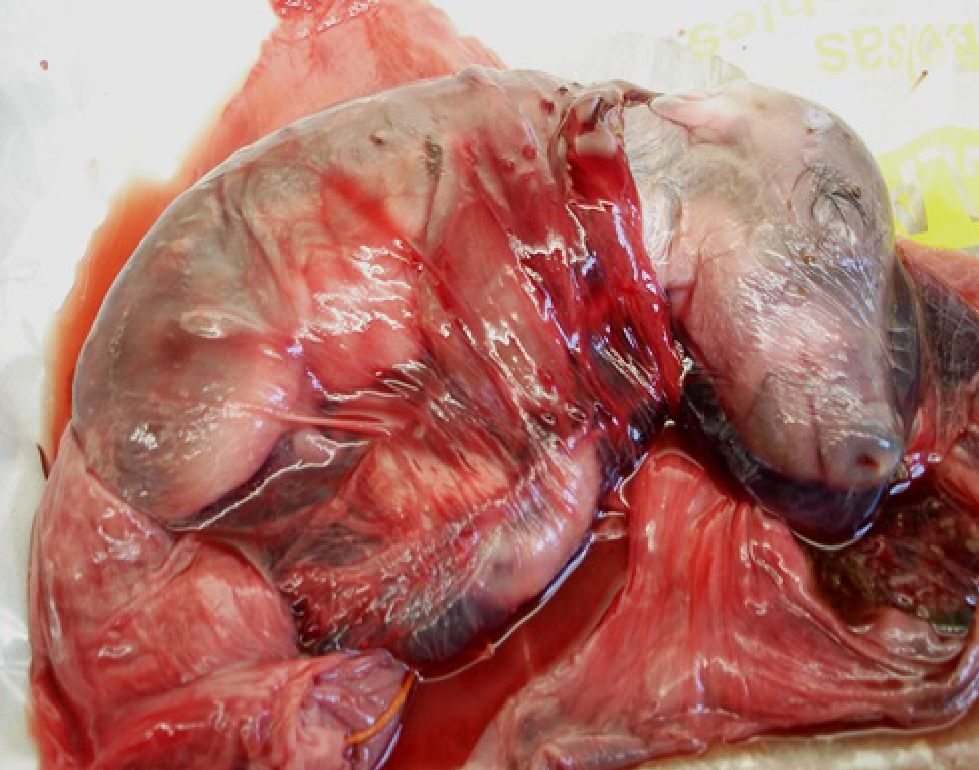
Figura 3
Feto jabalí abortado.
Este estudio fue financiado por el Proyecto Nacional INTA, AESA 202821.

Figura 1
Genotipificación MLVA.

Figura 2
Feto jabalí abortado.

Figura 3
Feto jabalí abortado.
