QUESOS ARTESANALES VENEZOLANOS: EVALUACIÓN DE LA CALIDAD BACTERIOLÓGICA E IDENTIFICACIÓN DE BACTERIAS ÁCIDO LÁCTICAS COMO COMPONENTES BACTERIANOS DE INTERÉS BIOTECNOLÓGICO
Venezuelan Artisanal cheeses: Assesment of bacteriological quality and identification of lactic acid bacteria as bacterial components of biotechonological interest
QUESOS ARTESANALES VENEZOLANOS: EVALUACIÓN DE LA CALIDAD BACTERIOLÓGICA E IDENTIFICACIÓN DE BACTERIAS ÁCIDO LÁCTICAS COMO COMPONENTES BACTERIANOS DE INTERÉS BIOTECNOLÓGICO
Revista Científica, vol. XXVI, núm. 2, pp. 65-70, 2016
Universidad del Zulia
Recepción: 26/10/15
Aprobación: 01/03/16
Financiamiento
Fuente: Fondo Nacional de Ciencia, Tecnología e Innovación (FONACIT)
Nº de contrato: N°2012000816
Fuente: Instituto Nacional de Nutrición y a la Universidad Nacional Experimental Sur del Lago “Jesús María Semprún”
Resumen: Se hicieron estudios microbiológicos en muestras de quesos artesanales producidos a pequeña escala en tres Estados de Venezuela. Aislados de ADN total de los quesos, suero y leche, fueron analizados con técnica de reacción en cadena de la polimerasa (PCR) simple y múltiple, empleando oligonucleótidos específicos para distintas especies bacterianas. Los resultados obtenidos evidenciaron la presencia de las bacterias ácido lácticas Lactobacillus fermentum, Lactobacillus delbrueckii subsp. bulgaricus y Streptococcus thermophilus, y la ausencia de bacterias patógenas como Listeria monocytogenes, Salmonella, Shigella y Escherichia coli en las muestras de cuajada y queso analizadas.
Palabras clave: Lactobacillus, Streptococcus, productos lácteos, PCR.
Abstract: Microbiological studies were performed on samples of artisanal cheeses produced at small scale in three Venezuelan States. Total DNA isolates from cheese, whey and milk, were analyzed with simple and multiple polymerase chain reaction (PCR) technique, employing oligonucleotides specific to several bacterial species. The obtained results prove the occurrence of the acid-lactic bacteria Lactobacillus fermentum, Lactobacillus delbrueckii subsp. bulgaricus and Streptococcus thermophilus, and the absence of pathogenic bacteria like Listeria monocytogenes, Salmonella, Shigella and Escherichia coli from curd and cheese samples studied.
Keywords: Lactobacillus, Streptococcus, dairy products, PCR.
INTRODUCCIÓN
La designación de queso artesanal se refiere a quesos elaborados a mano utilizando procedimientos pocos o no mecanizados, según usos y costumbres tradicionales que conservan maestros queseros calificados. A diferencia de aquellos elaborados industrialmente que usan leche pasteurizada, los quesos artesanales se preparan con leche cruda como materia prima. Como resultado, estos quesos son a menudo más complejos en sabor y variedad. Las diferencias sensoriales características de los quesos elaborados con leche cruda están relacionadas, entre otros factores, con las dinámicas microbianas particulares de cada uno. Las bacterias ácido lácticas como Streptococcus thermophilus, Lactobacillus delbrueckii subsp. bulgaricus y Lactobacillus fermentum son componentes esenciales para la producción de una amplia variedad de quesos italianos (Parmesano, pecorino, mozzarella, entre otros) [5]. El predominio de especies bacterianas en este producto resulta de una combinación de factores como son: 1) Las características propias de la leche cruda, relacionadas con la raza y nutrición del ganado que la produce , 2) la microbiota natural de las leches regionales y 3) los procedimientos empleados en su tratamiento [2,4]. Caracterizar la dinámica poblacional bacteriana de los quesos artesanales es un problema muy interesante desde el punto de vista teórico y tecnológico.
En Venezuela se han desarrollado diferentes tipos de quesos blancos artesanales: llanero, guayanés, de mano, telita, crineja o trenza, palmita, Santa Bárbara, criollo fresco y madurado. Es común en la elaboración artesanal e industrial de quesos el empleo de una mezcla comercial de enzimas cuyo principal componente es quimosina, también llamada “cuajo”. Dependiendo de la variedad, su contenido de sal puede ser moderado o alto, y sus texturas, suave, semi-dura y dura. Según datos de la Encuesta de Seguimiento al Consumo de Alimentos del Instituto Nacional de Estadística [7], la leche y el queso blanco son los lácteos más consumidos por la población venezolana. La caracterización de estos quesos constituye un paso inicial para extender su producción a mayor escala. Existe un reporte del aislamiento, identificación y caracterización de la flora láctica presente en el queso artesanal ahumado andino, en el cual se demuestra la presencia principalmente de bacterias ácido lácticas de los géneros Lactobacillus y Lactococcus [1]. En otro estudio, Rodríguez y col. [13], aislaron e identificaron bacterias del género Enterococcus a partir de queso ahumado andino, y evaluaron su potencial biotecnológico incluyendo este aislado en diferentes mezclas junto a Lactobacillus y Lactococcus como cultivos iniciadores, para la producción de un queso con las características sensoriales del producto artesanal, pero que la materia prima sea leche pasteurizada [13]. A pesar que el uso de leche cruda como materia prima conlleva un riesgo de contaminación por bacterias patógenas, en Venezuela no existen registros formales de brotes infecciosos asociados al consumo de quesos artesanales nacionales, aunque si se haya reportado la detección de los |patógenos Staphylococcus aureus y Escherichia coli O157:H7 en muestras de queso artesanal de cuatro Estados venezolanos [11].
Una manera rápida y eficaz de realizar la detección, identificación taxonómica y caracterización bacteriológica en los alimentos es la aplicación de métodos de biología molecular como la reacción en cadena de la polimerasa (PCR), dada su alta sensibilidad y especificidad. Esta herramienta analítica que permite indagar la composición bacteriana de los quesos, los componentes biotecnológicos derivados de su producción artesanal, y la detección temprana de patógenos .
El objetivo de esta investigación fue detectar por PCR simple, la presencia de las bacterias ácido lácticas Streptococcus thermophilus, Lactobacillus delbrueckii subsp. bulgaricus y Lactobacillus fermentum, así como descartar, a través de PCR múltiple, los patógenos Salmonella spp., Shigella spp., Listeria monocytogenes y E. coli en muestras de quesos artesanales venezolanos.
MATERIALES Y MÉTODOS
Cepas bacterianas y condiciones de cultivo
Se emplearon cinco cepas de referencia como controles positivos para verificar la amplificación específica con los oligonucleótidos utilizados en este estudio. Las cepas de referencia Streptococcus thermophillus (Centro Venezolano de Colecciones Microbianas CVCM 0649) y Lactobacillus delbrueckii subsp. bulgaricus (CVCM 1393), fueron crecidas en medio líquido MRS (DIFCO) y en MRS agar (DIFCO), a 37ºC en condiciones de microaerofilia. Las cepas de referencia Salmonella enterica subsp. enteritidis (Instituto Nacional de Nutrición-INN), Shigella flexneri (INN). Escherichia coli 0157:H7 (CVCM 0417) se cultivaron en medio LB líquido y sólido y Listeria monocytogenes (CVCM 446) en medio PALCAM (OXOID®). La presencia de L. fermentum se confirmó por la secuenciación de los productos de PCR obtenidos de cuatro muestras seleccionadas al azar en la Unidad de Estudios Genéticos y Forenses del Instituto Venezolano de Investigaciones Científicas ya que no se contaba con la cepa de referencia.
Análisis bacteriológico
En total, se recolectaron siete muestras de cuajada ( C ) y siete muestras de diferentes tipos de queso fresco (Q) provenientes de casas de familia, fincas y pequeñas empresas de producción artesanal. Diez en el municipio Miranda (C01, Q01, C02, Q02, C03, Q03, C04, Q04, C05 Y Q05) (Edo. Guárico), dos en el municipio Alberto Adriani (C06, Q06) (Edo. Mérida) y dos en el municipio Colón (C07, Q07) (Edo. Zulia). Los quesos fueron producidos utilizando como materia prima leche vacuna cruda (Guárico) y mezclas de leche cruda vacuna y bufalina (Mérida y Zulia), tratadas con cuajo comercial (Giber de Venezuela, C. A. ®). Las muestras de queso y cuajada escurrida se trasladaron al laboratorio en bolsas con cierre hermético a temperatura de refrigeración 4-8ºC, en cavas con hielo. Además, en cada una de las tres localidades se tomaron por triplicado muestras de suero drenado de la cuajada, tres (Sur del Lago) y tres (Mpio. Miranda- Edo. Guárico) usado para lavar el queso una vez prensado, y tres muestras de leche que sería destinada a la producción de queso: dos de ellas en el municipio Miranda-Edo. Guárico y una en el Sur del Lago-Edo. Mérida; todas las muestras obtenidas por sumergir el hisopo en suero o en leche se trasladaron embebidas en los medios de transporte Cary-Blair (OXOID®) y tiogliocolato (CONDA®) estas se mantuvieron a temperatura ambiente, por un tiempo máximo de una semana, para análisis bacteriológico posterior. Estos medios de transporte permiten la preservación de las muestras hasta por 45 días.
El análisis bacteriológico para la identificación de Salmonella y Shigella se llevó a cabo en un total de nueve muestras: tres de leche (Municipio Miranda-Edo.Guárico) y seis muestras de suero drenado (de tres fincas del Sur del Lago y tres muestras de dos fincas del municipio Miranda-Edo. Guárico, de una de las fincas se obtuvo suero drenado sin sal y también suero salado).
Las muestras de leche y suero se analizaron para detección de Salmonella spp. y L. monocytogenes mediante la aplicación de los protocolos descritos en las normas COVENIN 1291:1988 [10] y COVENIN 3718:2001 [9]. Adicionalmente, las colonias consideradas presuntivas fueron crecidas en caldo para identificación molecular posterior.
Aislamiento de ADN y reacción en cadena de la polimerasa (PCR)
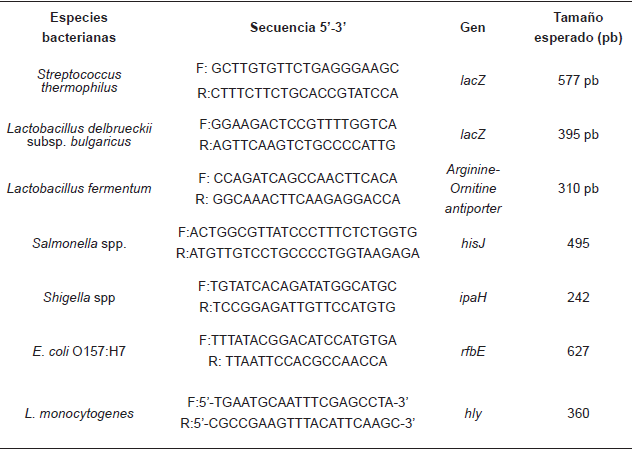
Las muestras de cuajada o queso (2 g) se homogeneizaron en una inyectadora estéril en 5-8 mL de buffer fosfato salino. Se tomó 1 mL de este homogenato y se aisló el ADN total empleando el método lítico, cuya eficiencia fue analizada en un estudio comparativo realizado por Quigley y col. [12]. El sedimento de las bacterias obtenidas de colonias presuntivas crecidas en caldo fue empleado para aislar ADN mediante el método físico de ebullición. Para la identificación de las bacterias ácido lácticas L. fermentum; L. delbrueckii subsp. bulgaricus y para S. thermophilus se emplearon oligonucleótidos especie-específicos [5] (TABLA I). Por otra parte, se procedió a detectar bacterias Salmonella spp. y Shigella spp., utilizando oligonucleótidos género-específico de acuerdo a He y col. [8], y en el caso de cepa E. coli O157:H7 y L. monocytogenes la detección se realizó con los oligonucleótidos especie-específicos, reportados por Yang y col. [14]. TABLA I. Se procedió al análisis por PCR múltiple, del ADN total extraído de 1) muestras de queso y 2) muestras de cuajada escurrida antes del salado. Todas las PCR se realizaron por triplicado. Los resultados de análisis de PCR múltiple para los patógenos Salmonella spp., Shigella spp. y E. coli O157:H7 también se confirmaron independientemente por PCR simple. La reacción de PCR estaba compuesta por: Buffer 5X, MgCl2 1,5 mM, ADN total (50-150 ng), dNTPs 200 μM, oligonucleótidos 0,4 μM, 1U de Flexi GoTaq ADN polimerasa (PROMEGA). Todos los ensayos se realizaron en un volumen de reacción total de 25 uL. Las condiciones de los ensayos de PCR fueron: 1) Para la detección de Salmonella spp., Shigella spp. y E. coli O157:H7: 95ºC (5 min), seguido de 35 ciclos: 95ºC (30 seg), 58ºC (45 seg), 72°C (1 min) , 2) Para la detección de S. thermophilus, L. fermentum y L. delbrueckiii subsp. bulgaricus :95ºC (5 min), seguido de 35 ciclos: 95ºC (30 seg), 58ºC (45 seg) 68°C (1 min), y 3) Para L. monocytogenes 95°C por 10 min seguido de 40 ciclos: 94ºC (30 seg), 50ºC (30 seg) 72°C (1 min) y finalmente un paso de extensión de 72ºC (10 min).
RESULTADOS Y DISCUSIÓN
Se observó que en dos muestras de fincas distintas, ambas del municipio Miranda, una de leche y otra de suero drenado, se aislaron colonias presuntivas para Salmonella spp. La presencia de este género bacteriano en las muestras de leche y suero también se detectó por PCR.
También a partir de dos muestras de suero drenado (una muestra del municipio Miranda-Edo Guárico y una muestra del municipio Alberto Adriani-Sur del Lago) se aislaron colonias presuntivas de L. monocytogenes, sin embargo, el análisis realizado por PCR no arrojó un resultado confirmatorio de la presencia de este patógeno en ninguna de éstas (resultados no mostrados).
En la totalidad de las muestras de cuajada y queso procesadas, el resultado negativo del análisis de PCR permitió descartar la presencia de Salmonella, Shigella y E.coli O157:H7. Se conoce que bacterias del género Lactobacillus, en particular cepas de las especies L. fermentum, L. gallinarum, L. rhamnosus y L. plantarum aisladas de productos lácteos, han demostrado potente actividad inhibitoria contra patógenos causantes de enfermedades entéricas (E. coli y Salmonella spp.) [2]. En el presente trabajo, en todas las muestras analizadas de queso y cuajada se identificaron bacterias ácido lácticas (TABLA II) S. thermophilus, L. fermentum (FIG.1) y L. delbrueckii subsp. bulgaricus (FIG. 2). Considerando que existen evidencias que demuestran que S. thermophilus produce una bacteriocina termolábil que exhibe actividad bacteriostática contra patógenos como Listeria monocytogenes y algunas especies de Bacillus [6], es posible postular que el predominio de bacterias ácido lácticas (Streptococcus, Lactobacillus, entre otros géneros) en este producto artesanal sea un factor determinante en la prevención de la proliferación de enteropatogenos.
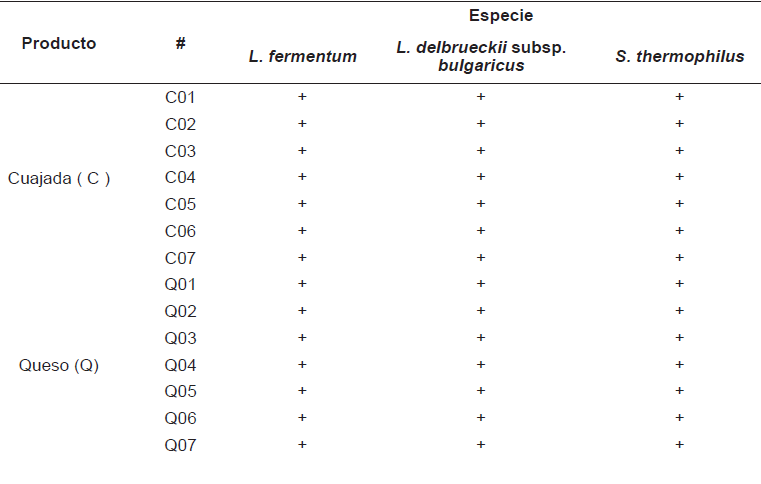
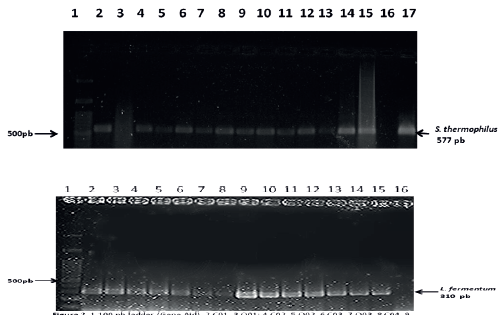
FIGURA 1 CORRIDA ELECTROFORÉTICA DE PRODUCTOS DE PCR Arriba : S. thermophilus y Abajo : L. fermentum. 1 100 pb ladder (Gene Aid), 2 C01, 3 Q01; 4 C02, 5 Q02; 6 C03, 7 Q03; 8 C04, 9 Q04; 10 C05, 11 Q05; 12 C06, 13 Q06; 14 C07, 15 Q07;16 CONTROL NEGATIVO,y 17 CONTROL POSITIVO S. thermophilus. C=CUAJADA y Q=QUESO. S.thermophilus 577 pb y L.fermentum 310 pb. Agarosa 1,5%. Tinción Diamond (PROMEGA)
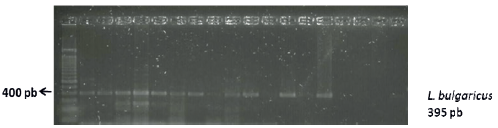
FIGURA 2. CORRIDA ELECTROFORÉTICA DE PRODUCTOS DE PCR L. delbrueckii subsp. bulgaricus. 1 100 pb ladder (INVITROGEN), 2 C01, 3 Q01; 4 C02, 5 Q02; 6 C03, 7 Q03; 8 C04, 9 Q04; 10 C05, 11 Q05; 12 C06, 13 Q06; 14 C07, 15 Q07;16 y17 vacios; 18 CONTROL NEGATIVO, 19 CONTROL POSITIVO. C=CUAJADA y Q=QUESO. Agarosa 1,5%. Tinción Diamond (PROMEGA)
CONCLUSIONES E IMPLICACIONES
El presente estudio establece la presencia de algunas especies de bacterias ácido lácticas de interés biotecnológico en quesos artesanales venezolanos. Además corrobora la especificidad de métodos moleculares para la detección tanto de bacterias ácido lácticas así como bacterias patógenas en alimentos.
Es posible sugerir el uso industrial de las bacterias ácido lácticas identificadas en este estudio para añadir cualidades sensoriales a quesos elaborados a mayor escala. Se recomienda ampliar este tipo de estudios a otros ámbitos de América Latina e integrar sinérgicamente resultados a nivel de toda la región para el establecimiento de estrategias de mejoramiento de la calidad de productos lácteos, que puedan ser difundidas adecuadamente a corto y mediano plazo entre sus productores.
Agradecimientos
Al Fondo Nacional de Ciencia, Tecnología e Innovación (FONACIT) como ente financiador del Proyecto PEII N°2012000816 titulado: «Caracterización Microbiológica de Leche y Productos Lácteos en los Estados Zulia y Guárico», al Instituto Nacional de Nutrición y a la Universidad Nacional Experimental Sur del Lago “Jesús María Semprún” por el apoyo en la recolección y procesamiento de muestras.
Referencias
[1] ALVARADO, C.; CHACÓN, Z.; OTONIEL, J.; GUERRERO, B.; LÓPEZ, G. Aislamiento, identificación y caracterización de bacterias ácido lácticas de un queso venezolano ahumado andino artesanal. Su uso como cultivo iniciador. Rev. Cientif., FCV-LUZ. XVII(3):301-308. 2007
[2] BERESFORD, T.P.; FITZSIMONS, N.A.; BRENNAN, N.L.; COGAN, T.M. Recent advances in cheese microbiology. Int. Dairy J. 11: 259-274. 2001.
[3] BUJNAKOVA, D.; KMET, V. Functional properties of Lactobacillus strains isolated from dairy products. Folia microbiol. 57: 263-267. 2012.
[4] CORROLER, D.; MANGIN, I.; DESMASURES, N.; GUEGUEN, M. An ecological study of lactococci isolated from raw milk in the camembert cheese registered designation of origin area. Appl. Environ. Microbiol. 64: 4729-4735.1998.
[5] CREMONESI, P.; VANONI, L.; MORANDI, S.; SILVETTI, T.; CASTIGLIONI, B.; BRASCA, M. Development of a pentaplex PCR assay for the simultaneous detection of Streptococcus thermophilus, Lactobacillus delbrueckii subsp. bulgaricus, L. delbrueckii subsp. lactis, L. helveticus, L. fermentum in whey starter for Grana Padano cheese. Int. J. Food Microbiol. 146: 207-211.2011.
[6] DELORME C. Safety assessment of dairy microorganisms: Streptococcus thermophilus. Int. J. Food Microbiol. 126(3):274-7. 2008.
[7] INSTITUTO NACIONAL DE ESTADÍSTICA (INE). Sociales: Encuesta de Seguimiento Al Consumo de Alimentos. Informe primer semestre 2014. En línea: http://www.ine.gov.ve/documentos/Social/ConsumodeAlimentos/pdf/ informeEsca.pdf. 39-40. 2015.
[8] HE, Y.; DAI, J.; LI, Y. Simultaneous and rapid detection of enteric pahogens from raw milk by multiplex PCR. World J. Microbiol. Biotechnol. 27: 2597-2602. 2011.
[9] COMISIÓN VENEZOLANA DE NORMAS INDUSTRIALES (COVENIN). Aislamiento e identificación de Listeria monocytogenes en alimentos. COVENIN 3718-2001. 2001
[10] COMISIÓN VENEZOLANA DE NORMAS INDUSTRIALES (COVENIN).Alimentos. Aislamiento e identificación de Salmonella spp. COVENIN 1291-88. 1988.
[11] MÁRQUEZ, J.G.; GARCÍA R., C.E. Microflora patógena del queso blanco “ telita” elaborado en cuatro estados de Venezuela. An. Venez. Nutr. 20: 17-21. 2007.
[12] QUIGLEY, L.; O’SULLIVAN, O.; BERESFORD, T.P.; PAUL- ROSS, R.; FITZGERALD, G.F.; COTTER, P.D. A comparison of methods used to extract bacterial DNA from raw milk and raw milk cheese. J. Appl. Microbiol. 113: 96- 105. 2012.
[13] RODRIGUEZ, M.E.; CHACÓN, Z.; GUERRERO, B.; OTONIEL, J.; LÓPEZ, G. Selección y elaboración de un cultivo iniciadora partir de cepas de Enterococcus aisladas de un queso venezolano ahumado andino. Rev. Cientif. FCV-LUZ. XVII (6): 641-646.2007
[14] YANG, Y.; XU, F.; XU, H.; AGUILAR, Z.P.; NIU, R.; YUAN, Y.; SUN, J.; YOU, X.; LAI, W.; XIONG, Y.; WAN, C.; WEI, H. Magnetic nano-beads based separation combined with propidium monoazide treatment and multiplex PCR assay for simultaneous detection of viable Salmonella Typhimurium, Escherichia coli O157:H7 and Listeria monocytogenes in food products. Food Microbiol. 34: 418-424. 2013.